4.1 Metodologia
La costruzione dei modelli biomeccanici utilizzati nelle simulazioni FEM sviluppate in questo studio, può essere divisa in fasi distinte ognuna delle quali utilizza un pacchetto commerciale apposito per la risoluzione di problemi specifici:
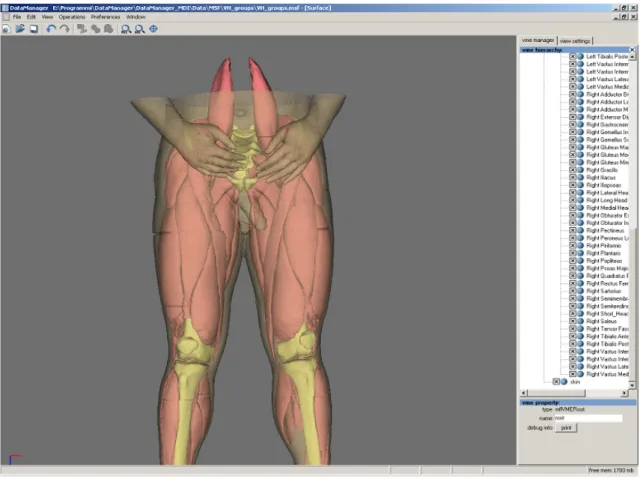
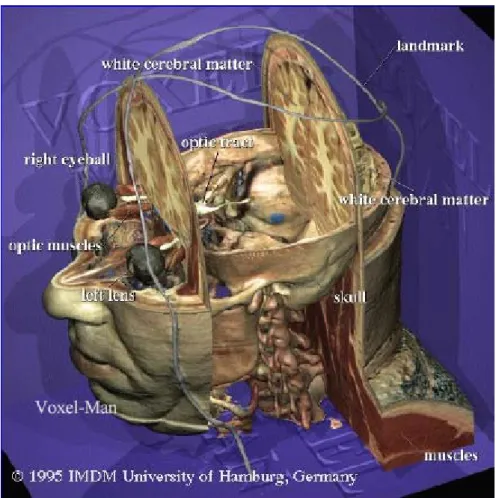
• Datamanager: software sviluppato dagli “Istituti Ortopedici Rizzoli” di Bologna utilizzato per estrarre tutte le superfici necessarie per la costruzione dei modelli biomeccanici, infatti all’interno di Datamanager sono disponibili superfici di pelle, ossa, tendini, legamenti e muscoli (Fig.4.1).Tali superfici provengono dal Visibile Human Project [1] (vedi paragrafo 4.2), dataset di immagini fotografiche e radiografiche di un intero cadavere.
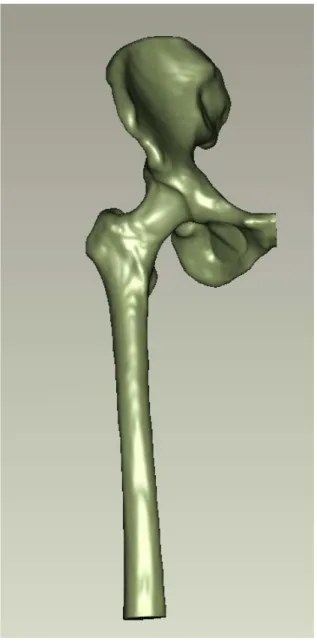
• Geomagic: software utilizzato nelle operazioni di reverse engeneering; permette di costruire il modello CAD in formato IGES partendo dalle superfici in formato STL estratte da Datamanager. Per costruire il modello CAD digitale le superfici vengono suddivise in patches che sono vere e proprie pezze parametrizzate mediante le quali si ha una rappresentazione di alto livello delle geometrie (Fig.4.2). Le patches rappresentano inoltre delle superfici di appoggio per le gli elementi della mesh.
• Unigraphics: programma CAD utilizzato nella costruzione dei volumi delimitati dalle superfici estratte nel modo suddetto.
• HyperMesh: software utilizzato per costruire la mesh solida; implementa l’algoritmo dell’advancing front che prevede la costruzione della mesh a strati partendo dalle mesh piane della frontiera. Tale procedura garantisce un’ottima ricostruzione dei contorni (massima boundary recover) mentre il condizionamento degli elementi peggiora all’interno del dominio. E’ l’algoritmo più utilizzato nei problemi di modellazione solida perché garantisce la miglior qualità dei risultati sui contorni che rappresentano le zone dove sono massimi i gradienti.
4.2 Superfici anatomiche: Visibile Human Project
Le superfici anatomiche utilizzate per costruire i modelli solidi derivano dal Visibile Human Project.
Nel 1988 durante un meeting sulle immagini anatomiche tridimensionali tenuto presso l’NLM (National Library of Medicine, USA), è nata l’idea di sviluppare un progetto finalizzato alla costituzione di un dataset che contenesse le immagini digitali di un corpo intero di uomo e di donna.
Nel 1994 l’NLM annunciava di essere in possesso di un dataset contenente immagini digitali del corpo di un uomo.
Dal momento che uno studio pilota, mostrava che le immagini provenienti da CT (tomografia computerizzata) e MR (risonanza magnetica) risultano distorte dal processo di congelamento venne fatta un’acquisizione sia prima sia dopo tale procedura.
L’acquisizione delle immagini venne eseguita a partire da 18 ore dopo la morte dell’uomo; le immagini di risonanza magnetica sono 256*256 pixel con 16 bit di risoluzione, mentre per la tomografia computerizzata (CT) le fette furono realizzate con spaziatura variabile da 1 a 5 mm.
Successivamente il cadavere fu conservato in una cella frigorifera tenuta a –7°C prima di eseguire nuovamente delle tomografie con incrementi di 1 mm.
Dalla camera frigorifera a –7 °C il cadavere fu spostato in una cella di congelamento a –70°C da dove venne rimosso dopo due giorni.
Il cadavere venne poi sezionato utilizzando un sistema di taglio appositamente sviluppato presso la Scuola di Medicina dell’Università del Colorado; la macchina di taglio era costituita da una sega circolare a controllo numerico sulla quale venne montato un disco da 14 pollici in diametro (355.6 mm).
Inizialmente il corpo fu diviso in quattro blocchi principali: il primo blocco comprendeva testa, collo e torace, il secondo addome e pelvi, il terzo la coscia e il ginocchio e l’ultimo le caviglie ed i piedi.
Ciascun blocco venne immerso in un mezzo gelatinoso che provvedesse una volta congelato a dare stabilità al blocco nella fase di taglio.
Appena la gelatina fu solida il blocco venne trasferito in una cella di congelamento mantenuta a –85 °C dove rimase per 12 ore prima di essere sezionato ad intervalli di 1 mm.
Ogni fetta venne fotografata a colori ottenendo delle immagini in formato TIFF (a 14-bit).Al termine di questa procedura il dataset contiene le seguenti immagini.
Immagini provenienti da MR
• Immagini assiali della testa e del collo spaziate di 4 mm • Immagini coronali del corpo intero spaziate di 4 mm
Sia quelle assiali che quelle coronali hanno dimensione: 256*256 pixel. Immagini provenienti da CT
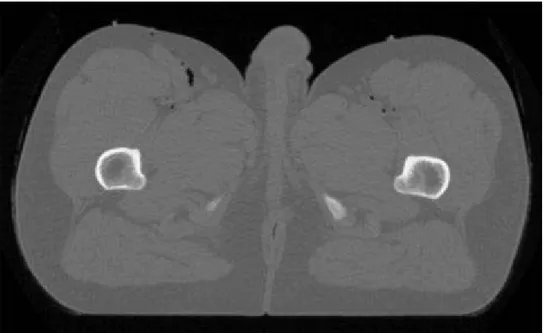
• Immagini assiali del corpo intero spaziate di 1 mm (512*512 pixel). Immagini Fullcolor
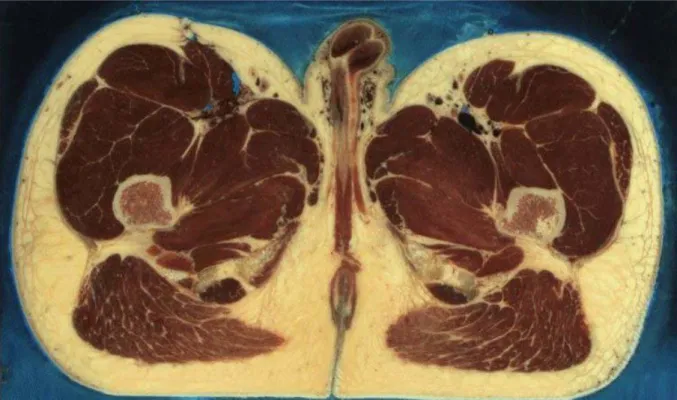
• Immagini assiali del corpo intero spaziate di 1 mm (2048*1216 pixel).
Le fotografie sono in formato TIFF (14 bit significativi per ogni canale RGB), mentre, le immagini radiologiche sono in formato raw (a livelli di grigio, 16 bit).
Si riportano a titolo di esempio un’immagine Fullcolor (Fig.4.3), due immagini CT (Fig.4.4 e Fig.4.5) e un immagine MRI (Fig.4.6)
Fig. 4. 4: Immagine CT prima del congelamento
Fig. 4. 6: MRI
L’accesso all’archivio può avvenire direttamente dalla rete mediante un FTP (protocollo di trasferimento di file) sul server dell’NLM.
L’archivio costruito è di fondamentale importanza nello sviluppo di modelli biomeccanici per simulazioni agli elementi finiti ma trova anche altre applicazioni:
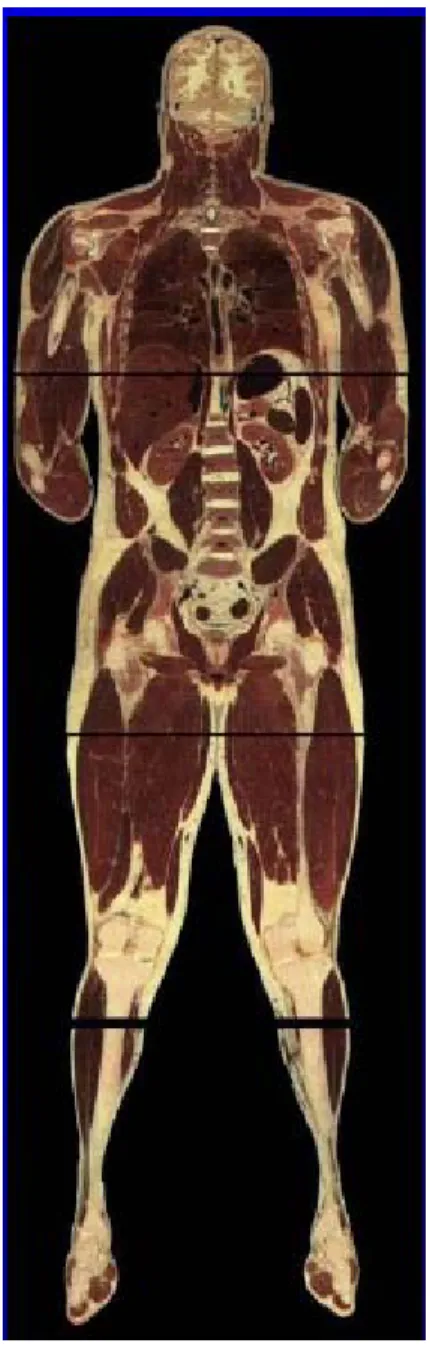
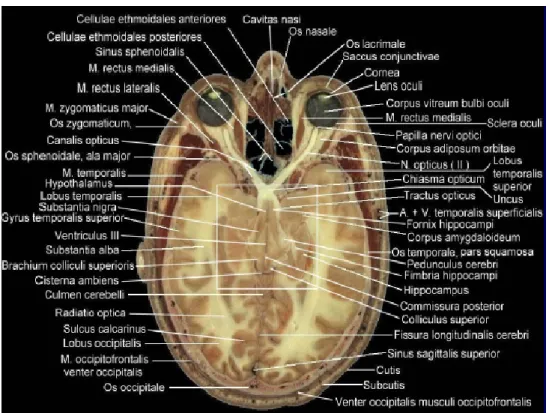
• Archivio anatomico 2D (Fig.4.8, Fig.4.9, Fig.4.10);
Fig. 4. 9: sezione assiale e descrizione anatomica
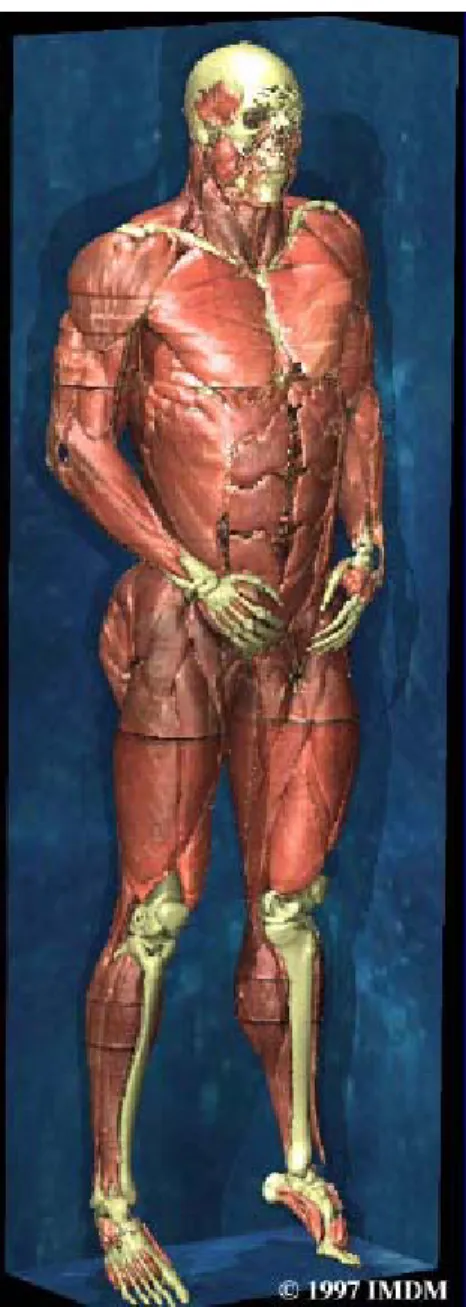
• Archivio anatomico 3D (Fig.4.11, Fig.4.12);
Immagini classificate
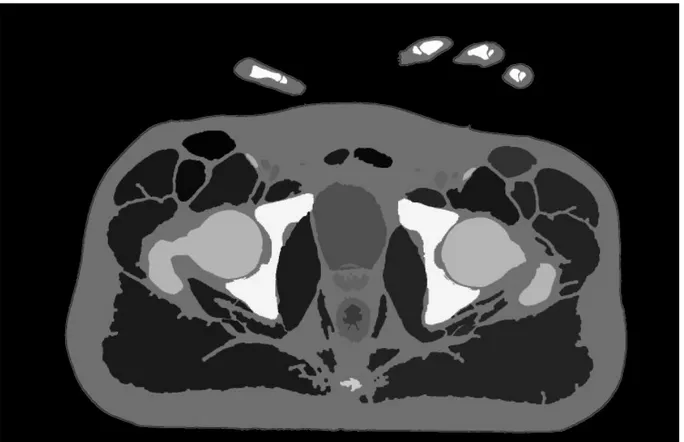
In un lavoro successivo le immagini Fullcolor sono state classificate. In particolare, le diverse strutture anatomiche (tra cui ossa, muscoli e tendini) sono state identificate e ad ognuna di queste è stato assegnato un valore specifico di livello di grigio. Si sono così ottenute delle nuove immagini a livelli di grigio in cui ogni livello corrisponde ad una determinata struttura anatomica (Fig.4.13).
Fig. 4. 13: rappresentazione della zona pelvica mediante livelli di grigio
Da tali immagini si sono ottenute le superfici delle strutture anatomiche tramite una sogliatura del livelli di grigio della struttura d’interesse.
I dati forniti dal Visibile Human Project sono stati utilizzati nel corso della tesi per ottenere: • La superficie esterna della pelle;
• La superficie di femore ed ileo destro;
• La superficie del rectus femoris e dei suoi tendini; • Lo spessore della pelle.