BIOTECNOLOGIE
Per
BIOTECNOLOGIE
si intendono tutte le pratiche finalizzate all’utilizzo di
organismi viventi o di processi biologici con lo scopo di ottenere prodotti
utili
•Biotecnologie antiche
– si selezionavano gli organismi viventi a seconda
delle caratteristiche che comparivano
naturalmente
•Biotecnologie moderne
– Si provvede direttamente al miglioramento
genetico deli organismi viventi attraverso
• Incroci selettivi
(si spostano da un organismo all’altro interi gruppi
di geni dalla funzioni ignote)
• Ingegneria genetica
(si spostano da un organismo all’altro singoli
geni dalla funzioni note
)
DNA RICOMBINANTE
L’ informazione genetica contenuta nel DNA è specifica per ogni individuo di una
specie.
Unendo porzioni di DNA di due individui diversi, si ottiene un organismo dotato di
un genotipo ibrido che manifesta nel fenotipo le caratteristiche di entrambi gli
individui di partenza. Questo esperimento è stato realizzato per la prima volta nel
1973
da due genetisti americani:
Cohen e Boyer.
I due ricercatori trasferirono in un
batterio di E. coli, i geni per la resistenza di due antibiotici, provenienti ciascuno da
ceppi di batteri differenti. Il nuovo batterio era in grado di resistere a entrambi gli
antibiotici.
Con il termine di Dna ricombinante si indica ogni molecola di Dna in cui sia
presente informazione genetica proveniente da due o più organismi differenti
Fu l’ inizio dell’era del DNA ricombinante
La tecnica del DNA ricombinante si basa sui seguenti presupposti:
•Uniformità del codice genetico
•Complementarietà delle basi
•Disponibilità di forbici e colla molecolari
•Possibilità di amplificare enormemente la quantità di DNA
•Possibilità di coltivare in vitro, le cellule
Questa rivoluzionaria tecnica biologica è stata messa a punto in
seguito alla scoperta:
•della transcrittasi inversa
•degli enzimi di restrizione
TRASCRITTASI
INVERSA
pag 249
Uno degli enzimi di restrizione più usati è EcoRI (si legge eco-erre-uno). La sigla si riferisce al batterio in cui l’enzima è stato trovato, al ceppo del batterio e al momento in cui è stato individuato. Eco dalle iniziali di Escherichia coli, R indica il ceppo RY13 e I specifica che si tratta della prima endonucleasi trovata in questo batterio.
Estremità coesive o sfalsate
Gli enzimi di restrizione tagliano il DNA, idrolizzando il legame fosodiesterico tra due nucleotidi adiacenti.
La caratteristica degli enzimi di restrizione è che tagliano il DNA in corrispondenza di sequenze palindromiche del Dna producendo dei frammenti chiamati frammenti di restrizione Gli enzimi di restrizione funzionano pertanto come delle forbici
Palindromo- Frase che ha lo stesso significato
-CTATAG--GAT
-CTA
TAG-ESTREMITA’ PIATTE
EcoRV
(ECO-ERRE-CINQUE)
SEPARAZIONE DEI FRAMMENTI DI RESTRIZIONE
TRAMITE ELETTROFORESI
Poiché ogni individuo ha una particolare sequenza di basi
azotate lungo il filamento di DNA, il numero e la
lunghezza dei filamenti cdi restrizione che si ottengono
usando lo stesso enzima di restrizione , varia da individuo
a individuo. Questo fenomeno è noto come
POLIMRFISMO DELLA LUNGHEZZA DEI FRAMMENTI D I
RESTRIZIONE (RIFLIP).
I frammenti di restrizione possono essere separati
mediante ELETTROFORESI
Jake and Ema's four children
were grown and had families of
their own. Jake was murdered.
Molti batteri presentano piccole molecole di DNA circolare esterne al DNA, chiamate
plasmidi
.
I plasmidi si duplicano in sintonia con il cromosoma batterico e questo li rende dei vettori
ideali per trasferire dei geni all’interno di una cellula ricevente.
A questo scopo i plasmidi batterici sono stati modificati in laboratorio per ottenere dei vettori
plasmidici. Tutti i vettori plasmidici contengono tutta una serie di elementi essenziali
•Un Ori (origine della duplicazione
- per consentire una duplicazione tutte le volte che si
verifica una divisione cellulare
•Un gene reporter (o gene marker)
- che contiene uno o più geni per la resistenza ad
antibiotici) per consentire di selezionare le cellule contenenti il vettore. Come plasmidi si
possono usare anche quelli che hanno come reporter il gene per la proteina verde
fluorescente (GFP) che emette luminescenza verde quando è colpita da luce ultravioletta.
•Un sito multiplo di clonaggio
- Che contiene un certo numero di sequenze di riconoscimento
per diversi enzimi di restrizione . Queste sequenze sono poste una vicina all’altra (nella figura
1 sono indicate dalla freccia) in una regione dove avverrà l’inserimento del DNA esogeno.
figura 1
LA TECNICA DEL DNA-RICOMBINANTE
PER COSTRUIRE UN DNA RICOMBINANTE , SI PROCEDE IN QUESTO MODO:
1.Procurarsi il DNA che contiene i geni che interessano
2.Procurarsi un vettore plasmidico
3.Tagliare il DNA ed il vettore plasmidico, entrambi con lo stesso
enzima di restrizione, in modo da ottenere delle estremità coesive
4.Unire insieme le estremità coesive del DNA e del plasmidio. Per
questo si ricorre all’ enzima DNA ligasi che come una ’’colla ‘’ è in
grado di ricostituire il legame fosfodiesterico tra due nucleotidi
adiacenti.
5.Inserire il plasmide ricombinante all’interno della cellula ricevente
6.Selezionare le cellule riceventi contenenti il plasmide per ottenere
Temperatura ottimale teorica: 37°C Temperatura ottimale reale: 4°-16°C
ESISTE IL PERICOLO DELLA RICIRCOLARIZZAZIONE
• Bassa concentrazione di DNA favorisce le ricircolarizzazioni
• Alta concentrazione di DNA favorisce il legame intermolecolare (inserto-vettore)
Riparate dagli enzimi della cellula ospite
La ricircolarizzazione si può evitare trattando il
vettore con fosfatasi alcalina per rimuovere i
gruppi fosfati
NICK
COME INSERIRE UN PLASMIDE RICOMBINANTE IN UNA CELULA RICEVENTE
L’ inserimento di un plasmide ricombinante in una cellula ricevente prende il
nome di
TRASFORMAZIONE
se la cellula è batterica o
TRASFEZIONE
se si tratta
di una cellula eucariotica.
Le principali tecniche per ottenere questo scopo sono le seguenti:
•SHOCK TERMICO
(per batteri) – Le cellule batteriche vengono immerse in un soluzione concentrata di ioni calcio a bassa temperatura (2-4 °C). Questi ioni, carichi positivamente si legano ai lipopolisaccaridi della parete batterica e attraggono il DNA che è negativo . La temperatura viene poi innalzata oltre i 40 °C e riportata velocemente a 2-4 °C . Questi shock termico provoca la dilatazione dei pori a livello della parete cellulare permettendo l’ingresso degli ioni calcio e quindidel vettore plasmidico.•ELETTROPORAZIONE
(per batteri e cellule eucariotiche) – Le cellule sono sottoposte per pochi secondi a un campo elettrico che alterando il potenziale elettrico di membrana provoca l’ apertura di canali che consentono l’ ingresso del vettore.•PISTOLA PER BOMBARDAMENTO BIOLISTICO
(per cellule vegetali) – I plasmidi da inserire vengono adesi a particelle di’ oro o tungsteno che poi vengono sparate attraverso la membrana cellulare , con una speciale pistola ad aria compressa, detta pistola genica•MICROINIEZIONE
(per cellule embrionali) – Il vettore plasmidico viene iniettato direttamente all’ interno della cellula grazie a un minuscolo ago di vetro utilizzato al microscopio con l’aiuto di uno speciale strumento: il micromanipolatorePISTOLA PER BOMBARDAMENTO BIOLISTICO
E’ necessaria una premessa. Per CLONAGGIO si intende la produzione di copie multiple di una data molecola; per
CLONAZIONE invece si intende la produzione di organismi geneticamente identici a quelli di partenza definiti CLONI. Per riconoscere tra i batteri quelli che effettivamente hanno incorporato il plasmide vettore, è sufficiente far crescere i batteri in corrispondenza dell’antibiotico specifico per il vettore utilizzato, dal momento che i vettori plasmidici contengono un gene marker per la resistenza a quello specifico antibiotico. Solo quelli che hanno incorporato il vettore e che quindi esprimono il gene per la resistenza, possono sopravvivere. In questo modo si ottiene un colonia batterica pura contenente il DNA esogeno. Tutte le volte che i batteri si dividono duplicano oltre che i loro geni anche quelli contenuti nel vettore. Da una singola cellula batterica, dopo 30 divisioni (circa 10 ore) si ottengono 230 cellule geneticamente identiche
(CLONAZIONE), corrispondenti a oltre un miliardo di copie del gene inserito, utili per l’analisi del gene stesso e la determinazione del suo prodotto (CLONAGGIO)
PLASMIDE RICOMBINANTE INSERITO IN BATTERI
FORMAZIONE DI COLONIE BATTERICHE
RICONOSCIMENTO DELLE CELLLULE TRASFORMATE E CLONAGGIO DEL DNA RICOMBINANTE
batteri
batteri
Batteri trasformati
batteri
Data l’elevata capacità di ricombinazione genetica da parte dei batteri c’è la probabilità di selezionare batteri che non hanno incorporato il plasmide, ma che sono diventati resistenti a quell’antibiotico per mutazione. In tal caso si può abbinare al marker per un antibiotico quello per la proteina verde fluorescente (GFP). I batteri trasformati, emettono una luminescenza verde quando sono illuminati da luce ultravioletta.
IMPIEGO DELL’ OPERONE-LAC PER UNA SELEZIONE PIU’ SICURA
Colonie non ricombinanti (blu) Colonie ricombinanti (bianche) Β-galattosidasi
Il plasmide contiene il gene selvatico (o wild type) lacZ+ che codifica la
beta-galattosidasi
, in grado di scindere il lattosio nei due monomeri glucosio e
galattosio.. All’interno di questo gene è presente il sito di clonaggio, in
corrispondenza del quale, avviene l’inserimento di DNA esogeno. Come si può
notare nella figura se un frammento di DNA viene inserito nella regione del sito
di clonaggio, si determina un’inserzione nel gene lacZ+; il codice di lettura per la
beta-galattosidasi viene interrotto e non può essere prodotta beta-galattosidasi
funzionale. Se una cellula batterica viene trasformata dal solo plasmide non
ricombinante, in presenza di
lattosio
e di un substrato cromogeno della
beta-galattosidasi, come l’
X-gal
(5-bromo-4-cloro-3-indolil-beta-galattoside), la
betagalattosidasi scinde l’X-gal in un prodotto colorato precursore dell’indaco. Le
colonie batteriche quindi assumeranno un colore blu. Se nel gene lacZ+ del
plasmide vettore è stato inserito del DNA estraneo, e quindi il vettore è diventato
un vettore ricombinante, le cellule batteriche trasformate non producono più
una betagalattosidasi. Pertanto in presenza di lattosio (l’induttore artificiale
dell’operone lac) e di X-gal, quest’ultimo in mancanza dell’enzima
beta-galattosidasi non può essere più trasformato nel precursore dell’indaco. Le
colonie batteriche quindi, trasformate con un vettore ricombinante, saranno
bianche
Trasferimento in E. Coli e riconoscimento dei
trasformanti
Assenza di lattosio nel mezzo significa assenza di espressione del transgene
Presenza di lattosio nel mezzo
significa espressione del transgene
La molecola del DNA ricombinante è formata da: 1.Gene umano per l’insulina (rosa)
2.DNA del plasmide (azzurro) che contiene
• gene marcatore resistenza alla penicillina (verde)
• promotore (nero) segnale regolativo che permette al gene di essere trascritto nelle cellula ospite
• gene interruttore operone lac (giallo)
Coltivazione trasformanti PLASMIDE
VIRUS COME VETTORI
Come vettori possono essere utilizzati anche i VIRUS BATTERIOFAGI che svolgono un ciclo litico come il batteriofago lambda. Nel genoma di questi fagi si introduce un sito di clonaggio per un ‘enzima di restrizione ,in modo da consentire di saldare all’interno del genoma virale il DNA esogeno. Il vantaggio offerto dai batteriofagi lambda, è quello di poter ospitare frammenti di DNA più lunghi rispetto ai vettori plasmidici. Il gene esogeno non viene integrato, ma si comporta nelle cellule infetta come un plasmidio.
Per inserire stabilmente un gene all’interno del genoma della cellula ricevente si utilizzano i RETROVIRUS che sono in grado di integrare il loro genoma all’interno del genoma della cellula infettata
CICLO LITICO
5
5’
ESONE
ESONE
ESONE
3’ AAAAA
mRNA maturo
FIG. 2
FIG. 3
COME ISOLARE I GENI DA CLONARE
Premessa :geni discontinui e splicing libro biologia pag267-268
TRADUZIONE
COME ISOLARE I GENI DA CLONARE
Adesso che si sa come preparare una molecola di DNA ricombinante,
bisogna spiegare
come si fa ad isolare un frammento di DNA che contiene il
gene da clonare.
In merito sono necessarie alcune premesse.
I geni degli eucarioti sono discontinui; a porzioni codificanti dette
esoni
si
alternano porzioni non codificanti dette
introni
(vedi fig .2). Durante la
trascrizione vengono trascritti sia gli esoni che gli introni. Pertanto l’ mRNA
che si ottiene non può essere subito tradotto. A tal fine deve subire un
processo di maturazione ;
è necessario cioè che gli introni vengano rimossi.
Attraverso un processo chiamato di
SPLICING
(fig.3) gli introni vengono
tagliati e gli esoni vengono cuciti insieme. Al termine dello splilcing all’
esremità 3’ del filamento di mRNA si aggiunge una sequenza di 200 nucleotidi
A (coda poli A) con l’intento di facilitare il legame con i ribosomi.
Fatte queste premesse appare evidente che il
DNA genomico (il DNA del
nucleo)
non è il materiale ideale per isolare i geni. I geni infatti non sono
maturi perché contengono ancora gli introni.
Conviene pertanto partire dagli
mRNA maturi
dal momento che questi rappresentano i geni (circa il 5%) che
effettivamente sono espressi dalla cellula di un tessuto;
e i geni espressi
variano da tessuto a tessuto
COME ISOLARE GLI mRNA DA UNA CELLULA
Per isolare gli mRNA da una cellula si sfrutta la presenza alla loro estremità 3’ della coda poli A. Dapprima le cellule vengono frammentate in modo da liberare tutti gli acidi nucleici. Gli mRNA contenuti nell’estratto cellulare vengono messi in una colonna di separazione che contiene una resina a base di agarosio in cui sono presenti dei pezzetti di DNA a singolo filamento detti oligonucleotidi la cui sequenza è costituita solamente da timine (poli T). Gli oligonucleotidi poli T si appaiano alla coda poli A degli mRNA trattenendoli nella resina mentre gli altri acidi nucleici vengono eliminati con un lavaggio. Successivamente con l’aggiunta di un tampone gli mRNA purificati si staccano dalla resina e dai poli T e possono essere così recuperati.
IL PASSO SUCCESSIVO È QUELLO DI COSTITUIRE UNA GENOTECA O LIBRERIA DI cDNA
CELLULE
DNA genomico
(30000 geni)
taglio con enz. di restr.
Frammenti di DNA genomico
Molecole di DNA ricomb.
GENOTECA GENOMICA
Costituita da tanti cloni ognuno contenente un diverso frammento di DNA
si isola mRna totale presente in una cellula Trascrittasi inversa
Gli mRNA sono copiati in cDNA (a doppio filamento dalla trascrittasi inversa. I geni così ottenuti corrispondono al DNA maturo privato dagli esoni
Molecole di DNA ricomb
GENOTECA di cDNA
Costituita da tanti cloni contenente ciascuno un diverso cDNA. E ’diversa da tessuto a tessuto
Plasmidi PlasmidI
Introduzione plasmidi In batteri.
Selezione e clonaggio
GENOTECHE
•GENOMICHE
- contiene i geni ottenuti da tutto il DNA di un
cellula, anche quelli che non sono espressi . I geni non sono
maturi perché contengono ancora gli introni.
•di cDNA
- contiene solo i geni che si esprimono in una
cellula (circa il 5%) ottenuti a partire da mRNA maturo. I geni
sono privi di introni La biblioteca ottenuta sarà diversa per
ogni tipo di tessuto
LE SONDE PESCANO I cDNA NELLE GENOTECHE
(pag 173-174)
Cercare un singolo cDNA dentro una genoteca è come cercare un libro in una biblioteca senza catalogo, in cui i libri sono mescolati tra loro senza alcun ordine preciso
I cDNA vengono «pescati» usando come «esca» una sequenza nucleotidica (detta sonda)
complementare a quella del gene interessato
Le sonde sono pezzi di DNA o RNA a filamento singolo, naturali o artificiali, lunghi da 10 a 1000 nucleotidi, complementari ad una sequenza dei nucleotidi del gene che si vuole trovare e con il quale si ibridano.
cDNA ATTGACTTGATCAAGGCTA sonda TAACTGAACTAGTTCCGAT
Per renderla facilmente individuabile, la sonda viene marcata con isotopi radioattivi o con sostanze fluorescenti.
Volendo estrarre un gene specifico dalla genoteca, basterà mescolare la massa di cDNA con una certa quantità della sonda radioattiva che pescherà il cDNA voluto ibridandosi con esso.
L’allestimento della sonda implica la conoscenza a priori della sequenza del gene.
Se questa non è nota si parte dalla proteina e sfruttando il codice genetico si risale dalla sequenza amminoacidica alla corrispondente sequenza di nucleotidi.
Con tale sequenza si può costruire una sonda sintetica con cui pescare nella genoteca,PROTEINA DETERMINARE LA SEQUENZA
AMMINOACIDICA
SINTETIZZARE LA SONDA SETACCIARE UNA GENOTECA
• Sulla superficie di una piastra Petri, contenenti le colonie di una libreria cDNA, viene appoggiato un filtro di niitrocellulosa.
• Alcune cellule della colonia aderiscono al filtro che successivamente viene immerso in una soluzione in grado di lisare le cellule e liberare gli acidi nucleici. • Il DNA che ha carica negativa, rimane attaccato al filtro carico positivamente.
Il DNA così esposto viene quindi denaturato per separare i due filamenti
• A questo punto si introduce la sonda che si ibriderà con il CDNA specifico
• Poiché il filtro è una specie di fotografia della piastra da cui deriva, dalla posizione della sonda è possibile identificare quali cellule contenevano il cDNA che stiamo cercando. Le cellule sono prelevate e fatte moltiplicare in modo da ottenere una coltura pura.
Sonda radioattiva a DNA marcata con 32P
A contatto con il filtro la sonda si ibrida con il cDNA specifico
ISOLAMENTO DEL cDNA TRAMITE IBRIDAZIONE SU COLONIA
Trattasi di una variante del SOUTHERN BLOTTING
Sonda radioattiva cDNA
ATTGACTTG
TAACTGAAC
Filtro di nitrocellulosa Carico positivamenteISOLAMENTO DEL DNA TRAMITE TECNICA DEL SOUTHERN BLOTTING
L’ intero genoma viene tagliato con enzimi di restrizione. I frammenti di restrizione vengono separati in base alla grandezza per elettroforesi
I frammenti di DNA vengono denaturati (95°C) e trasferiti su
un foglio di nitrocellulosa.
.
Foglio di nitrocellulosa
Sonda radioattiva a DNA marcata con 32P
N,B. Se il materiale da isolare è RNA e non DNA la tecnica è
sostanzialmente la stessa e per analogia viene chiamata NORTHERN BLOTTING
Questa tecnica prenede il nome dal suo ideatore il biologo britannico Edwin. Southern
Con il termine blotting si intede il trasferimento e l’immobilizzazione di acidi nucleici da un gel o una soluzione acquosa a un supporto solido, generalmente una membrana di nitrocellulosa o nylon.
Premessa duplicazione del DNA
REAZIONE A CATENA DELLA DNA POLIMERASI (PCR)
LA DUPLICAZIONE PROCEDE IN DIREZIONE 5’ – 3’
REAZIONE A CATENA DELLA DNA POLIMERASI (PCR)
La PCR è una tecnica che permette di ottenere molte copie di un gene
Prima dello sviluppo di questa tecnica (ideata dal chimico Kary Mullis nel 1985). L’unico metodo per ottenere molte copie di un gene era il clonaggio del DNA, che comporta come si è visto, l’inserimento di un gene in cellule batteriche che a loro volta replicano il gene quando si dividono.
Il processo della PCR si svolge invece in una singola provetta, mescolando semplicemente il DNA con una serie di reagenti e ponendo il tutto in un termociclatore.
Questo apparecchio mediante una serie ripetuta di di riscaldamento e di raffreddamento permette di ottenere in poche ore , partendo anche da una piccola quantità di DNA milioni di copie di un gene.
Questa tecnica richiede la presenza di: •Porzione di DNA che ci interessa
• I quattro desossiribonucleotidi del DNA( A, G, T, C) •Primers
•DNA polimerasi resistente al calore ricavata dal batterio Thermus aquaticus (Taq)
Per eseguire la PCR si usa qualunque porzione del Dna, di cui devono essere note le sequenze iniziali e finali, perchè in queste posizioni vanno inseriti i primers.
I primers sono piccoli filamenti di DNA, complementari alle sequenze d’ inizio dello stampo che provvedono a dare inizio al processo dal momento che la DNA polimerasi non è in grado da sola di sintetizzare ex novo filamenti di DNA
Un ciclo PCR consiste di tre tappe:
1.Denaturazione. Il DNA è scaldato a 94 °C per 5 minuti. A questa temperatura il Dna si denatura e i due filamenti si separano provvedendo ciascuno a fungere da stampo per la sintesi di nuovo DNA
2.Ibridazione. La temperatura del termociclatore viene abbassata a 40-45°C per permettere ai due primers di legarsi alle sequenze d’inizio. I primers delimitano la regione di DNA che deve essere copiata.
3.Estensione . La DNA polimerasi sintetizza la regione di DNA compresa tra i due primers ad una temperatura di 72 °C. Come DNA polimerasi si usa quella del batterio Thermus aquaticus perché non si denatura alle alte temperature.
PCR (POLYMERASE CHAIN REACTION)
DNA Replication
PCR
DENATURING
DNA Helicase
Temperature
ANNEALING
RNA Primers
DNA Primers
EXTENSION
DNA Polimerase
Taq Polimerase
APPLICAZIONI DELLA PCR
• Applicazioni in criminologia perché permette di utilizzare anche
frammenti infinitesimali di DNA
• Per identificare la presenza di agenti infettivi come i virus dell’
HIV, della epatite e del papilloma virus
in particolare permette di identificare in modo precoce il
virus dell’HIV all’interno delle cellule umane, a differenza della
diagnosi tradizionale che basandosi sulla presenza degli
anticorpi dà responsi settimane se non mesi dopo il contagio.
• Per identificare piccole mutazioni dei geni responsabili di
tumori o di malattie come la fibrosi cistica, l’ anemia falciformre la
fenilchetonuria, la distrofia muscolare
SEQUENZIAMENTO DEL DNA CON IL METODO DI SANGER
Confronto fra dNTP e ddNTP
La DNA polimerasi procede in direzione 5’ 3’ aggiungendo
desossiribonucleotidi all’estremità 3' dell’ ultimo nucleotide inserito.
Se l’ultimo nucleotide inserito, fosse un didesossiribonucleotide, l’assenza del gruppo –OH in posizione 3’, impedirebbe la formazione del legame fosfoestere e di conseguenza l’aggiunta di un altro nucleotide alla catena in crescita. Pertanto la sintesi si arresterebbe nella posizione in cui all’estremità in crescita è stato aggiunto il didesossinucleotide
SEQUENZIAMENTO DEL DNA
pag.179 (pag 302 Biologia)Per sequenziare un tratto di DNA occorrono:
• Frammenti denaturati del tratto di DNA da sequenziare • DNA polimerasi
• Primers
• I quattro desossiribonucleosidi trifosfati
• i quattro didesossiribonucleosiditrifosfati ciascuno legato ad una sostanza fluorescente che emette una luce di diverso colore
ADENINA – GIALLO TIMINA – VERDE GUANINA – BLU CITOSINA - ROSSO
+
-5’
GENOMICA
Grazie alla possibilità di sequenziare il genoma è nata una nuova branca della
biologia molecolare: la genomica. Data l’enorme quantità di dati da elaborare e
visualizzare, questa nuova scienza si basa sulla bioinformatica.
Si riconoscono vari ambiti della genomica:
•
Genomica funzionale
– si prefigge lo scopo di determinare tutti i geni che
costituiscono il genoma di un specie
•
Genomica comparativa
– si prefigge di confrontare il genoma di due più specie
per definire i rapporti di parentela tra le specie stesse.
•
Metagenomica
– si occupa dell’analisi dei genomi d tutte le specie presenti in
un determinato ambiente al fine di determinarne la variabilità gennetica ossia
la biodivesità.
PROGETTO GENOMA UMANO
Il
Progetto genoma umano
(HGP, acronimo di Human Genome
Project) è stato un progetto di ricerca internazionale il cui obiettivo
principale era quello di determinare la sequenza delle coppie di basi
azotate che formano il DNA e di identificare e mappare i geni del
genoma umano.
Il progetto è stato completato il 22 giugno 2003 dal Genome
Bioinformatics Group della UCSC, composto da Jim Kent, Patrick
Gavin, Trrence Furey e David Kulp. Inoltre fu sostenuto da
Renato
Dulbecco
genetista premio Nobel ottenuto nel 1975.
Il sequenziamento del DNA umano ha riservato alcune sorprese:
•Il genoma umano è costituito solo per il 2 % da sequenze codificanti
pari a 21000 geni, molti meno rispetto agli 80000 – 15000 ipotizzati
• Il restante 98 % è costituito da DNA di cui non si conosce ancora a
fondo la funzione anche se ormai sembra coinvolto in processi di
regolazione.
•Mediamente i geni umani sono lunghi 27000 paia di basi azotate
•I geni non sono distribuiti uniformemente nel genoma. Ad es il
cromosoma 19 è densamente popolato di geni,mentre il cromosoma
8 ne è largamente sprovvisto
SONDE di DNA
POZZETTO
MICROARRAY
A livello pratico si procede in questo modo:
1.In laboratorio si sintetizzano oligonucleotidi a singolo filamento (sonde) che hanno una sequenza complementare a quella di ciascun gene del genoma Questa sequenza funge da etichetta del gene che lo identifica in maniera univoca. Queste sonde, nella quantità di pochi picogrammi (1 pg = 10 -12 ), vengono inserite in pozzetti (spot) presenti su sottili
supporti di silicio (microarray o Gene chip) di 1,5 cm di larghezza, 1,5 cm di lunghezza e 1 mm di spessore. Un microarray appare quindi come una griglia con migliaia di spot, in ciascuno dei quali c’è una sonda che corrisponde a un gene. Un microarray può contenere tutti i 20000 geni del genoma umano
TRANSCRITTOMICA E TECNOLOGIA MICROARRAY DI DNA
Benché tutte le cellule contengano lo stesso patrimonio genetico, soltanto alcuni geni vengono espressi a seconda di quale tessuto la cellula entra a far parte.
La trascrittomica è quella branca delle biologia molecolare che ha lo scopo di determinare quali geni e in che quantità, sono espressi in un determinato momento nelle cellule di un determinato tessuto.
cDNA mRNA
cDNA
cDNA a singolo filamento
Marcati con un gruppo fluorescente denaturazione Transcrittasi inversa Applicazione al microarray MARCATORE FLUORESCENTE IBRIDAZIONE TRA SONDA E cDNA
2. Dal tessuto che si vuole analizzare si estraggono gli mRNA che sono convertiti in cDNA tramite la transcrittasi inversa. Di seguito sono denaturati per convertirli in filamenti a singola elica e
marcati con un gruppo fluorescente. Infine sono applicati al microarray
3. Ciascun cDNA si ibrida alla sonda presente sul microarray con la sequenza a lui complementare. CELLULA
La lettura del microarray pemette quindi di stabilire quali geni sono espressi in
un dato momento nelle cellule di un determinato tessuto. Inoltre,
dall’intensità della fluorescenza è possibile stabilire l’ entità dell’espressione.
4. Illuminando il microarray con un raggio laser, i pozzetti corrispondenti alla presenza di un cDNA legato alla sua sonda , emettono radiazioni fluorescenti
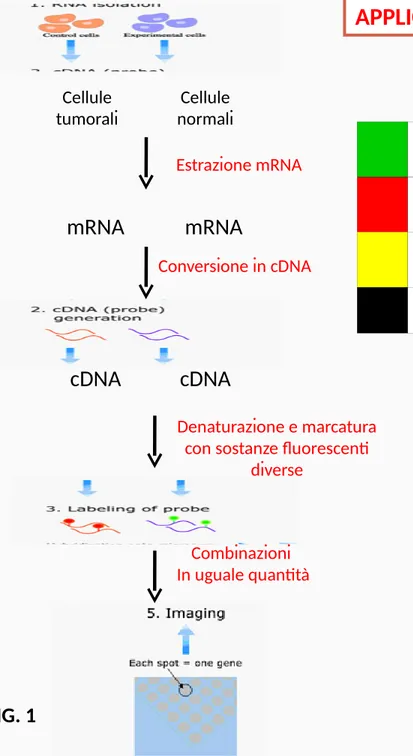
Cellule normali Cellule tumorali mRNA mRNA cDNA cDNA Denaturazione e marcatura con sostanze fluorescenti
diverse
Ibridazione con le sonde della griglia Estrazione mRNA
Conversione in cDNA
Combinazioni In uguale quantità
Leucemia mieloide acuta Leucemia linfoide acuta APPLICAZIONI DELLA TECNOLOGIA DEI MICROARRAY DI DNA
FIG. 1 geni espressi tessuto normale geni espressi tessuto tumorale geni espressi in entrambi i tessuti geni non espressi
La tecnologia dei microarray trova diversi campi di applicazione in medicina, soprattutto nella diagnostica dove ad esempio si confronta l’espressione genica in un tessuto tumorale rispetto ad uno sano.
La figura 1 mostra come confrontare l’espressione genica in due tipi cellulari diversi : cellule tumorali (rosse) , cellule normali (azzurre)
La preparazione del microarray richiede i seguenti passaggi. 1.Isolamento dell’mRNA dai due campioni cellulari.
2.Conversione in cDNA tramite transcrittasi inversa
3.Denaturazione e marcatura dei cDNA con marcatori fluorescenti (fluorocromi); rosso per le cellule tumorali, verde per le cellule normali
4.Il cDNA delle cellule tumorali, viene mescolato in egual quantità con il cDNA delle cellule normali. La miscela è versata sul microarray e lasciata incubare per 12 ore a 42 °C in modo che possa avvenire l’ibridazione tra le molecole di cDNA e le sonde
5.Dopo 12 ore il microarray è lavato per eliminare i cDNA che non si sono ibridati.
6.Con uno scanner si analizza il microarray. Si può notare che gli spot hanno diverso colore a. Spot luminosi verdi – corrispondono ai geni espressi in un tessuto normale
b. Spot luminosi rossi – corrispondono ai geni espressi in un tessuto tumorali
c. Spot luminosi gialli – corrispondono ai geni espressi in un tessuto normale e normale d. Spot luminosi neri – corrispondono ai geni non espressi .
7.Analisi.
Il tumore è dovuto a mutazioni a carico dei geni che controllano la divisione cellulare. Sapere quali geni si esprimono in una forma tumorale aiuta a capire il meccanismo di formazione neoplastica.
Differenti tipi di cancro esprimono gruppi di geni diversi. La tecnologia microarray aiuta a diagnosticare il tipo di tumore cui è affetto un paziente e quindi di scegliere tempestivamente la terapia più adeguata.
PROTEOMICA
La
proteomica
si prefigge lo scopo di determinare le proteine (
proteoma
) che
costituiscono l’espressione genica di una cellula. L’ analisi del proteoma consiste
nelle seguenti fasi:
•Estrazione delle proteine per centrifugazione
•Separazione delle proteine per elettroforesi - si sfuttano le differenti cariche
elettriche delle proteine
Proteina nativa
Carica netta - 4
Proteina trattata con SDS
Carica netta
-Un organismo che si trova ad avere nel proprio genoma un gene proveniente da
un’ altra specie, viene chiamato
organismo transgenico
, mentre il gene estraneo
è detto
transgene
.
Qualunque organismo il cui genoma sia stato modificato dall’ingegneria genetica,
non necessariamente per l’ aggiunta di un gene estraneo è detto organismo
geneticamente modificato o
OGM
• BIOTECNOLOGIE AGRARIE
• BIOTECNOLOGIE AMBIENTALI
• BIOTECNOLOGIE MEDICHE
APPLICAZIONI DELLA TECNICA
DEL DNA-RICOMBINANTE
BIOTECNOLOGIE
AGRARIE
PIANTE TRANSGENICHE
Se si prende un frammento del
tessuto di una pianta e lo si mette in
un terreno di coltura in presenza di
giusti
ormoni,
si
ottiene
una
masserella di cellule indifferenziate
detta
CALLO
Questo se coltivato in opportune
condizioni ambientali, darà origine ad
una pianta geneticamente identica
alla pianta madre.
Se nelle cellule del callo, prima della
rigenerazione si introducono alcuni
geni esogeni, si ottiene una pianta
transgenica
Per trasferire nuovi geni nelle piante si utilizza un particolare plasmide, detto
plasmide Ti
derivato dal batterio patogeno vegetale
Agrobacterium tumefaciens.
Quando questo batterio aderisce a una cellula vegetale, trasferisce al suo
interno una porzione del proprio plasmide Ti
(detta T-DNA)
integrandola nel
cromosoma della pianta. Il T-DNA contiene geni che inducono la proliferazione
delle cellule infette , generando tumori nella pianta colpita.
Nel T-DNA del plasmide Ti viene inserito ,ricorrendo agli enzimi di restrizione ,un DNA esogeno
(fig. 1, 2, 3). Il plasmide Ti-ricombinante è introdotto in cellule di Agrobacterium tumefaciens prive del plasmide Ti naturale (Fig. 4). A questo punto, infettando con l’ A. tumefaciens le cellule del CALLO, il gene inserito nel t-DNA, insieme a questo sarà trasferito e integrato nel cromosoma della cellula (fig.5-6). Da queste cellule trasformate si possono ottenere dei cloni di piantine tutte geneticamente identiche, contenenti il gene esogeno
GOLDEN RICE
ESEMPI DI PIANTE TRANSGENICHE
Piante ad elevato contenuto nutrizionale
Golden rice- La vitamina A è una vitamina presente in molti alimenti; quali carote, uova burro. Questa vitamina, svolge un ruolo importantissimo nella visione e nella differenzazione cellulare. Il riso , cereale alla base dell’alimentazione in vaste aree dell’ Asia, e tuttavia povero di Vitamina A . La conseguenza è che in India e in estremo oriente, 250 milioni di bambini soffrono di carenza di vitamina A, una condizione che causa 2 milioni di decessi all’anno ed è una delle principali cause di cecità infantile. Nel 2000, utilizzando A. tumefaciens è stato creato un riso transgenico contenente due geni per la sintesi della vitamina A che si accumula nei chicchi conferendo loro un caratteristico colore dorato da cui il nome Golden rice,
Piante che producono oli ricchi di acidi grassi polinsaturi ω 3
Patate con un contenuto solido maggiore, in modo d’ assorbire meno olio durante la frittura
Bacillus thuringensis
Piante resistenti ai parassiti (piante Bt)
Il batterio Bacillus thuringensis, un comune abitatore del suolo, contiene un gene detto gene cry
che codifica per una proteina tossica nei confronti di molti insetti parassiti. La tossina è specifica per le larve d’insetto, mentre è innocua per i vertebrati oltre che per insetti benefici come le api. Con la tecnica precedentemente descritta il gene cry è stato inserito in molte piante di interesse agricolo tra cui mais , cotone , riso, ecc.
Le piante transgeniche che esprimono il gene cry, dette piante Bt, sono quindi resistenti a molti parassiti, con il vantaggio immediato che non serve più utilizzare i pesticidi chimici per proteggere i raccolti.
E’ il più noto alimento transgenico molto più produttivo di quello naturale grazie alla presenza del gene cry che produce una tossina che uccide le larve di lepidotteri parassiti del mais
N2 + 8H+ + 8e- + 16 ATP → 2NH
3 + H2 + 16ADP + 16 Pi
L’ USO DELLE RELAZIONI COOPERATIVE NATURALI
ossia simbiosi tra piante e batteri azotofissatori o tra piante e funghi
Noduli radicali
ALTRE APPLICAZIONI IN CAMPO AGRARIO
• L’ allevamento animale • Fermentazioni
BIOTECNOLOGIE
AMBIENTALI
BIORISANAMENTO
L’ utilizzo di microorganismi per la rimozione di sostanze inquinanti presenti nell’ambiente è detto biorisanamento
IL CASO DELLA EXXON VALDEZ. Il 24 marzo 1989 la superpetroliera Exxon valdez, naufragò in prossimità delle coste
dell’Alaska, riversando in mare 40000 metri cubi di petrolio che contaminarono l’area costiera per 1500 Km. Per risanare il mare si fece ricorso non soltanto alle normali tecniche di risanamento (barriere, idrovore, ecc) ma si decise di sfruttare alcune specie di batteri geneticamente modificati, in particolare PSEUDOMONAS PUTIDA , in grado di utilizzare come fonte di carbonio, molti composti organici inquinanti presenti nel petrolio. Pseudomonas putida appartiene alla categoria dei batteri estremofili , capaci di vivere in condizioni ambientali estreme (geyser con tempetature prossime ai 100 gradi, laghi e mari molto salati, miniere ricche di minerali tossici, ecc.) Gli enzimi che permettono loro di vivere in condizioni così estreme sono chiamati estremozimi
BIOFILTRI I metalli pesanti come mercurio piombo, cadmio rilasciati dagli scarichi industriali, sono tra gli inquinanti più pericolosi e difficili da eliminare. Per questo sono allo studio batteri geneticamente modificati, in grado di rimuovere tali sostanze. Per esempio in batteri come E. coli, sono stati inseriti alcuni geni, provenienti da un batterio che permettono di assorbire mercurio attraverso la membrana cellulare. Ai batteri è stato introdotto anche il gene per la metallotionina , una proteina in grado di fissare il mercurio all’interno della cellula. I batteri ingegnerizzati, possono poi essere immobilizzati su un supporto solido per creare dei biofiltri in grado di assorbire il mercurio presente nell’acqua .
BIOSENSORI Sono batteri in grado di rilevare la presenza di inquinanti nell’acqua o nel suolo. A questo scopo si usano batteri ingegnerizzati con il gene per la proteina fluorescente verde GFP proveniente dalle meduse e con un promotore che si attiva solo quando nel mezzo di coltura è presente solo un certo inquinante . Pertanto quando la proteina viene sintetizzata il batterio diventa luminescente. Con questa tecnica sono stati realizzati biosensori per la rilevazione di metalli pesanti e idrocarburi.
GFP PROMOTORE
PRODUZIONE DI COMPOST
Il compostaggio è una delle più comuni applicazioni biotecnologiche industriali.
Si definisce compostaggio la trasformazione mediante fermentazioni, della frazione umida dei rifiuti solidi urbani e degli scarti della lavorazione agricola in terriccio, detto compost, da usare come fertilizzante.
• Nella prima fase del processo, intervengono i batteri mesofili, che lavorando a temperature comprese tra 25 °C e 45 °C, operano l’ ossidazione aerobica del materiale organico.
• Quando la temperatura degli strati interni supera i 50°C e l’ ambiente è saturo di CO2 , intervengono i batteri termofili anaerobi, che completano la fermentazione.
• A questa fase segue il processo di maturazione in cui sono coinvolti soprattutto i funghi che operano la demolizione delle sostanze più complesse come la lignina e le cellulosa e portano alla formazione del compost.
BIOCOMBUSTIBILI
Un’ alternativa ai combustibili fossili è rappresentata dai biocombustibili come il bioetanolo e il biodiesel , sintetizzati attraverso processi fermentativi di masse vegetali.
I biocombustibili hanno un impatto ambientale pressoché nullo in quanto liberano solo la CO2 fissata durante la vita della pianta e non quella intrappolata migliaia di anni fa.
Il bioetanolo si ottiene per fermentazione degli zuccheri a partire da mais, sorgo, canna da zucchero, legno di recupero, paglia, ecc. Il biodiesel si ottiene per raffinazione di oli vegetali come quello di colza, di soia di palma.
Una fonte particolarmente conveniente per la produzione di bioetanolo è rappresentata dagli scarti della lavorazione del legno, dalla paglia , dalla buccia dei frutti. Queste biomasse sono ricche di carboidrati, ma presentano anche molecole complesse a struttura fibrosa e molto resistenti alla decomposizione come la lignina e la cellulosa.
Per rendere sfruttabili questi scarti, è necessario, prima demolire queste sostanze liberando gli zuccheri di cui sono composti,.
A tal fine si sono creati dei batteri ingegnerizzati in cui si sono potenziate le vie enzimatiche di degradazioone la cellulosa e la lignina.
BIOMASSE
Paglia , rifiuti lavorazione legno, eccIDROLISI
ENZIMATICA
Si ottiene glucosioFERMENTAZIONE
ETANOLO
batteri ingegnerizzatiBIOTECNOLOGIE
MEDICHE
Produzione di insulina da parte di batteri per curare
il diabete di tipo I dovuto ad una produzione insufficiente di insulina
mRNA insulina
traduzione
sequenza segnale
serve per la secrezione dell’ ormone all’esterno
A
C
B
Preproinsulina
(inattiva)
INSULINA
COME VIENE PRODOTTA L’ INSULINA NELLE CELLUE UMANE
A
BL’ mRNA dell’insulina comprende il messaggio di quattro parti distinte della proteina:
•Sequenza segnale •Catena A
•Catena C •Catena B
Se forniamo ai batteri il gene dell’insulina, questi si attengono scrupolosamente
alla traduzione letterale del messaggio, formando preproinsulina inattiva
PORZIONE DI DNA CHE CODIFICA
PER CATENA A
PORZIONE DI DNA CHE CODIFICA
PER CATENA B
Ricombinazione con plasmidi
e inserzione in E. coli
Estrazione catena A Combinazione e sintesi Estrazione catena B
ANTICORPI MONOCLONALI – MAB
• circa 7000/mm
3
• FAGOCITI
• LINFOCITI
GRANULOCITI
•Presenza di grossi granuli
visibili dopo colorazione
•si dividono in:
•Neutrofili
(
coloranti neutri)•Eosinofili
(coloranti acidi)•Basofili
(coloranti basici)•
MONOCITI
•sono i più grandi
• LINFOCITI B
• LINFOCITI T
LINFOCITI
risposta specifica (anticorpi)
LINFOCITA B
LINFOCITA T
•
Gli anticorpi sono proteine che riconoscono una specifica combinazione di
amminoacidi detta epitopo presente su di una proteina estranea (es. la proteina
di rivestimento esterno di un virus) che costituisce l’antigene
LINFOCITI B (bone marrow) -
IMMUNITÀ DI TIPO UMORALE
•I linfociti B (bone marrow) rimangono nel midollo osseo dove maturano
•agiscono all’esterno della cellula (gli anticorpi non possono entrare
all’internodi una cellula)
LINFOCITI T (da timo) - IMMUNITÀ DI TIPO CELLULARE
• I linfociti T (da timo) maturano nel timo
per trasferirsi dopo la loro maturazione nei linfonodi.
• Uccidono personalmente le cellule
COME SI PRODUCONO GLI
ANTICORPI MONOCLONALI
antigene milza IBRIDOMA Milstein Kohler Cellula tumorale di mieloma un tumore cheinteressa i linfociti B
Da ogni singolo ibridoma si può far sviluppare un clone di cellule che producono un unico tipo di anticorpo detto monoclonale
Da ogni ibridoma è anche possibile isolare il gene corrispondente a quell’anticorpo per inserirlo in altri organismi, per esempio le piante di tabacco per a produzione su larga scala
In ambito diagnostico
• Test di gravidanza – grazie ai MAB è possibile rilevare nelle urine la presenza della
gonadotropina corionica , l’ormone secreto dall’embrione al momento
dell’annidamento.
• Immunoscintigrafia
IMPIEGO DEGLI ANTICORPI MONOCLONALI IN MEDICINA
IMMUNOSCINTIGRAFIA Grazie alla scintigrafia è possibile vedere le zone dove si accumulano gli anticorpi marcati, identificando la presenza e la collocazione del tumore.
Nell’ambito della ricerca
•Microscopia a immunofluorescenza
Utilizzando i Mab è stato possibile marcare le
proteine che costituiscono i microtubuli del
fuso mitotico e seguire dettagliatamente la
sua formazione.
Nell'uomo la sintesi della struttura cellulare per la corretta ripartizione dei cromosomi nelle cellule uovo, il fuso mitotico, richiede un tempo molto elevato e sfrutta meccanismi leggermente diversi rispetto ad altre specie. Questa differenza spiega perché nella nostra specie c'è un tasso relativamente elevato di anomalie cromosomiche, che spesso portano ad aborti spontanei. Nella mitosi il fuso mitotico è sintetizzato da un'apposita struttura, il centrosoma, che però manca nelle cellule uovo di diverse specie, fra cui la nostra, dove è sostituito dai cosiddetti centri di organizzazione dei microtubuli (MTOC). Melina Schuh e colleghi, hanno ora scoperto che nell'uomo il fuso non è sintetizzato neppure dai MTOC, ma direttamente dai cromosomi. Questo meccanismo di sintesi è però molto più lento: mentre nel topo (in cui intervengono i MTOC) la creazione del fuso e il suo corretto posizionamento richiede 3-5 ore, nell'uomo si arriva alle 16-17 ore. Ciò fa sì che per 6-7 ore il fuso in formazione sia instabile: i microtubuli non sono abbastanza lunghi da agganciarsi al citoscheletro, ma lo sono abbastanza da potersi aggrovigliare. Se ciò avviene uno o più cromosomi possono essere tirati nella cellula figlia sbagliata. determinare trisomie come la sindrome
di Down
In ambito terapeutico
•
Terapia tumorale.
Sulla superficie delle cellule tumorali sono presenti degli
antigeni che non compaiono sulle cellule sane.
L’ anticorpo monoclonale specifico
per l’antigene tumorale
viene associato a delle molecole killer che dopo il
riconoscimento della cellula cancerosa entrano nel suo interno provocandone la
morte, senza danneggiare le cellule sane circostanti.
•
Immunizzazione passiva
- si intende la protezione immediata e di breve durata
verso le infezioni, ottenuta mediante la somministrazione di anticorpi sotto forma
di immunoglobuline o di antisieri. neonati di madri infette HBsAg positive (la
somministrazione avviene viene effettuata immediatamente dopo il parto o entro
le prime 12 h, combinata con la prima dose di vaccino.
TERAPIA ANTICANCRO CON GLI
ONCOREPRESSORI
Il 9% delle donne che ereditano un allele mutante BRCA1 ha il 60% di probabilità di di sviluppare un tumore al seno entro i 50 anni, percentuale che sale all’82% entro i 70 anni. Di contro nelle donne che hanno ereditato due alleli normali la percentuale di rischio è del 2%
Tramite la manipolazione genetica si potrebbe col tempo far in modo che la cellula riattivi un gene oncorepressore mutato in modo che si torni ad avere le due coppie normali.
BRCA1 è l’oncorepressore del
carcinoma ovarico-mammario
TERAPIA GENICA
Lo scopo della terapia genica è quello di sostituire i geni mancanti o difettosi con geni normali.
Un esempio è dato dall’ ADA-SCID ( Severe Combined Immuno Deficiencies) una grave malattia dovuta alla mancata produzione da parte dei globuli bianchi, dell’enzima
adenosina deaminasi (ADA). Quando manca l’ ADA, nell’organismo si accumulano tossine endogene che portano alla distruzione del sistema immunitario. In simili condizioni, lo organismo non è più in grado di difendersi infezioni banali, come un semplice raffreddore , che possono risultare mortali. La terapia ha dato timidi successi, l’unico inconveniente è che i vettori retrovirali, integrano il gene esogeno in posizioni casuali del genoma. Questo fatto può risultare un problema perché potrebbe bloccare l’espressione di un gene o alterarne la regolazione. Per questo motivo, si sono progettati vettori virali basati sul virus adeno-associato che integra il proprio genoma in un
punto ben definito sul cromosoma 19 che porta il gene ADA
1. Si prelevano cellule del midollo osseo che presentano la copia non funzionante del geneADA
2. Un retrovirus è ingegnerizzato attraverso l’inserzione del gene ADA funzionante
GENE NON SILENZIATO GENE SILENZIATO
TECNOLOGIA ANTISENSO
Un altra malattia genetica che si sta tentando di curare con la terapia genica di sostituzione è la COREA DI HUNTINGTON una malattia genetica neurodegenertiva che colpisce la coordinazione muscolare e porta ad un declino cognitivo e a problemi psichiatrici. Esordisce tipicamente durante la mezza età; è la più frequente malattia a causa genetica nei quadri clinici neurologici con movimenti involontari anomali (che prendono il nome di còrea).
È molto più comune nelle persone di discendenza europea occidentale rispetto a chi è di origine asiatica o africana. La malattia è causata da una mutazione autosomica dominante in una delle due copie di alleli di un gene codificante una proteina chiamata huntingtina, Attualmente, però, i migliori risultati vengono dalla tecnologia antisenso che porta allo spegnimento del gene.
La tecnologia antisenso è usata per il silenziamento di alcuni geni al fine di evitare che esprimano le informazioni di cui sono portatori.
LE CELLULE SAMINALI NELLA TERAPIA GENICA
Un particolare tipo di terapia genica prevede l’impiego delle cellule staminali.
Le cellule staminali sono cellule primitive, non specializzate, dotate della capacità di
trasformarsi in diversi altri tipi di cellule del corpo attraverso un processo denominato
differenziamento cellulare.
Le cellule staminali vengono classificate in quattro gruppi principali:
• Staminali unipotenti
- possono dare origine a
un solo tipo
di cellula. Per esempio, nel
midollo osseo esistono cellule staminali che sono in grado di dare origine solo ai globuli
rossi e non ai globuli bianchi.
• Staminali multipotenti
- che possono dare origine
ad alcuni tipi
di cellule. Sempre nel
midollo osseo, esistono delle cellule staminali da cui si originano più tipi di staminali
unipotenti (per esempio, quelle che danno origine ai globuli rossi e quelle per i vari tipi di
globuli bianchi).
• Staminali pluripotenti
- originano tutti tipi di tipi di cellule MA NON POSSONO DARE
ORIGINE A UN INTERO ORGANISMO; sono un esempio di staminali pluripotenti le cellule
dell’ embrione nello stadio di blastula e del cordone ombelicale.
• Staminali totipotenti
- originano tutti tipi di tipi di cellule E POSSONO DARE ORIGINE A
UN INTERO ORGANISMO; sono un esempio di cellule staminali totipotenti le cellule
dell’embrione nello stadio di 4 cellule (morula).
CELLULE STAMINALI ADULTE EMATOPOIETICHE
Le cellule staminali unipotenti e multipotenti sono chiamate cellule staminali adulte (SSC) perché si
trovano anche i diversi tessuti dell’ individuo adulto. Le cellule staminali ematopoietiche del midollo
osseo, per esempio, possono essere differenziate in tutti i tipi cellulari delle linee linfoide e mieloide. Le cellule staminali pluripotenti e totipotenti sono chiamate cellule staminali embrionali (ESC)
CELLULE STAMINALI PLURIPOTENTI INDOTTE (Ipsc)
Oggigiorno è possibile isolare e coltivare in laboratorio sia le SSC che le ESC da cui poter
ottenere diversi tipi di cellule se non interi organi.
Poiché l’ applicazione delle SSC è limitata l’ attenzione degli scienziati si è concentrata
sulle ESC.
Ora per ottenere cellule staminali pluripotenti è necessario sacrificare gli embrioni e nel
caso si tratti di embrioni umani questo comporta notevoli problemi di carattere etico.
Nel 2006 il ricercatore giapponese
Shinya Yamanaka,
premio Nobel per la Medicina nel
2012, mise a punto la tecnica per ottenere
cellule pluripotenti indotte (iPSC)
da cellule
adulte.
La tecnica prevede di
invertire il programma di differenziamento,
riportando le cellule già
differenziate a uno stato pluripotente simile a quello delle ESC.
Per ottenere questo scopo, si deve:
•introdurre nelle cellule adulte i geni per
4 fattori trascrizionali
caratteristici delle ESC.
L’espressione di questi geni causa il
de-differenziamento cellulare.
•Le iPSC possono poi essere fatte re-differenziare in tipi cellulari diversi da quello di
partenza.
CELLULE STAMINALI PLURIPOTENTI INDOTTE
3. Attraverso n vettore si introducono nelle cellule adulte i geni per 4 fattori trascrizionali caratteristici delle ESC. L’espressione di questi geni causa il
Le iPSC lasciano ben pensare ad un loro promettente impiego nella terapia genica
Come esempio si consideri una malattia del fegato chiamata
alfa-1.
Alfa 1 è causata da una mutazione recessiva. Come risultato, una proteina prodotta
nel fegato, e di solito rilasciata nel corpo per proteggerlo da danni, rimane
intrappolata nel fegato dove causa cirrosi. Alfa-1 è una delle malattie genetiche più
comuni e colpisce circa una persona su 2000. L'unico trattamento disponibile al
momento è il trapianto di fegato che è un importante intervento chirurgico che
tuttavia
implica prendere farmaci per tutta la vita per evitare il rigetto
dell'organo.
Per ovviare a questo inconveniente, i ricercatori hanno combinato la tecnologia
delle cellule staminali
iPSC
con la terapia genica.
Hanno preso delle cellule dalla pelle di un paziente con alfa-1 e le hanno
riprogrammate in cellule staminali
iPSC
.
Hanno poi corretto i difetto genetico inserendo il gene funzionale ed infinele hanno
trattate trattate per farle differenziare cellule del fegato.
Come cellule del fegato, hanno fatto un perfetto lavoro incluso una normale
produzione e rilascio della proteina sana.
LE CELLULE STAMINALI SONO ALLA BASE DELLA MEDICINA RIGENERATIVA
Le cellule staminali possono essere utilizzate, oltre che nella
terapia genica, anche per rigenerare tessuti danneggiati.
Ad esempio possono essere utilizzate :
•
Nei trapianti per sostituire cellule malate (ad es. le staminali
ematopoietiche vengono utilizzate per rigenerare il midollo in
pazienti affetti da leucemia).
•
Per rigenerare tessuti sani da impiantare nell’ospite al posto
di quelli malati (ad es. per curare il morbo di Parkinson o il
Diabete).
•
Per riparare tessuti danneggiati (ad es. la pelle ustionata o il
Su un gel di collagene si dispongono dei fibroblasti; le cellule del tessuto connettivale che producono la matrice extra cellulare. Su questo strato che funge da derma vengono fatte crescere delle cellule epidermiche.
Al posto del gel di collagene si utilizzano dei supporti polimerici.
epidermide
CLONAZIONE
DI MAMMIFERI
La pecora Dolly
1996
CLONAZIONE PRO E CONTRO
PRO
•Possibilità di ottenere un numero illimitato di copie con caratteristiche
identiche; caratteristica importante in zootecnia
•Salvaguardia e diffusione di specie minacciate dall’estinzione
•Possibilità di stabilire confronti tra animali con lo stesso patrimonio genetico nel
campo della patologia, dell’alimentazione , della farmacologia, ecc. (es quando si
testerà un farmaco in vivo si potrà sapere esattamente come agisce perché gli
animali trattati e quelli di controllo hanno la stessa fisiologia.
CONTRO
•Scarsissima possibilità di successo
•Danni al DNA con rischio di aumento di tumori o diminuzione della durata della
vita
Gli animali transgenici sono utilizzati in campo biomedico per:
• Utilizzare un mammifero come bioreattore per la
produzione di proteine umane
• Studiare la funzione di geni specifici
Per modificare un animale dal punto di vista genetico si possono
utilizzare due tecnologie
• Micro iniezione di uova fecondate
• Manipolazione di cellule staminali embrionali (ESC)
TOPO FEMMINA
Introduzione per microiniezione del retrovurus
contenente il gene per il fattore VIII per la coagulaz. sangue, ormone della crescita, ecc) e sua incorporazione nel DNA della cellula ospite
UOVO IMPIANTATO NELLA MADRE ADOTTIVA
TOPO MASCHIO
TOPI TRANSGENICI cellula uovo fecondataMICROINIEZIONE DI UOVA FECONDATE
produzione del fattore VIII della coagulazione
RETROVIRUS ingegnerizzato
Dopo la nascita i topi vengono esaminati per verificare che il loro genoma contiene il gene per il fattore VIII. Il fattore VIII sarà prelevato dal sangue
I II III VIII coagulo COAGULAZIONE DEL SANGUE IV
Dopo i topi, queste tecniche sono state estese ad altre specie animali. Per
esempio sono state generate
mucche transgeniche
, in grado di produrre latte
umanizzato, ovvero contenente
lisozima
,
lattoferrina
(proteina globulare
multifunzionale con attività antimicrobica, sia battericida che fungicida) e
alfa-lattalbumina
(proteina che attiva i processi protettivi e assorbitivi intestinali,
mediante queste azioni modula lo sviluppo cerebrale) umane; questo latte, ha
quindi proprietà nutritive molto simile a quello materno.
Un’ applicazione molto interessante è il
PHARMING
che consiste nel creare,
utilizzando le tecniche dell’ingegneria genetica piante e animali transgenici che
producono proteine
di interesse farmacologico
. Ad esempio:
•Sono state create pecore il cui latte contiene alte quantità di ormone della
crescita umano, usato per curare patologie legate a ritardi della crescita nei
bambini.
•Sono state create piante di tabacco, di mais e di soia transgenici che producono
anticorpi umani utili nella cura di molte patologie (infezioni virali, cancro). In altri
casi le piante transgeniche, producono altre molecole come l’enzima
glucocerebrosidasi
, utilizzato nella terapia di una malattia neurodegenerativa; la
sindrome di Gaucher.
Prelievo di cellule ES da una blastula di topi marroni
Inserimento delle cellule ES In un embrione di topi bianchi
Inserimento del gene (verde) con un marker per la resistenza ad un antibiotico (rosso) nelle cellule ES
Selezione delle cellule ES trasfezionate
La balastocisti viene impiantata in una madre sostitutiva
Per avere un topo che porti l’allele in tutte le sue cellule i topi chimera si incrociano tra loro
MANIPOLAZIONE DELLECELLULE STAMINALI EMBRIONALI ES (Forme chimeriche).
Le parti del topo con pelo marrone discendono dalle cellule ES del topo marrone e contengono il transgene, le parti del topo con pelo bianco derivano dalla blastocisti del topo bianco