4. RISULTATI
4.1 ANALISI COMPARATIVA DEI PRECURSORI
MIELO-MONOCITARI DI TOPI WILD TYPE E Otx1
-/-Studi precedenti effettuati nel laboratorio in cui ho svolto il lavoro di tesi hanno rivelato che Otx1, oltre ad avere un importante ruolo nell’eritropoiesi, è espresso anche nei precursori bipotenti di granulociti e macrofagi (Levantini et al., 2003). Per individuare il ruolo di Otx1 nell’ambito del lineage mielo-monocitario ho per prima cosa effettuato un confronto fra i precursori ematopoietici di topi wild type
e knock-out (Otx1-/-) attraverso saggi clonogenici in terreno semisolido.
I precursori ematopoietici sono morfologicamente indifferenziati, eterogenei e non possono essere tutti isolati come sottopopolazioni omogenee sulla base dell’espressione di specifici antigeni di membrana. Quindi vengono studiati sfruttando la loro capacità clonogenica in saggi effettuati in vitro. Colture in
terreno semisolido consentono l’analisi contemporanea sia di precursori
pluripotenti che di progenitori della serie eritroide, mielo-monocitaria e megacariocitaria, a diversi stadi di differenziazione.
Le cellule midollari prelevate dai femori di animali wild type e Otx1-/- sono state
coltivate in metilcellulosa ad una concentrazione di 100.000 cellule per piastra, e in presenza di fattori di crescita quali SCF, IL3 ed Epo. Al secondo giorno di coltura, si sviluppano piccole colonie eritroidi derivanti da precursori tardivi (CFU-E). A partire dal settimo giorno di coltura si osserva la formazione di diversi tipi di colonie: cloni originati da precursori eritroidi precoci (BFU-E); colonie contenenti granulociti e/o macrofagi derivate da precursori bipotenti
(CFU-GM) o da progenitori unipotenti (CFU-G,CFU-M); colonie miste contenenti diversi tipi di cellule mature (eritrociti, granulociti, macrofagi e, talvolta, megacariociti), derivate da precursori pluripotenti (CFU-Mix). In primo luogo ho valutato il numero di precursori mieloidi totali (CFU-GM + CFU-G +
CFU-M) in topi wild type e Otx1-/- sia di un mese che di sette mesi, in quanto i
knock-outs presentano in età pre-puberale una diminuzione degli ormoni GH, LH e FSH che determina nanismo e ipogonadismo. Tuttavia tale fenotipo è transitorio in quanto viene pienamente recuperato dopo il quarto mese di vita. I saggi clonogenici effettuati su midolli di mutanti di diversa età hanno dimostrato che nei topi nulli di un mese la quantità di precursori mieloidi totali subisce una lieve diminuzione rispetto ai wild type (Fig.4.1a). Tuttavia lo stesso tipo di studio condotto su midolli di topi a sette mesi di vita non ha evidenziato differenze
quantitative fra precursori mieloidi wild type e Otx1-/-. Pertanto il calo dei
precursori mieloidi sembra essere un’alterazione transiente (Fig.4.1b).
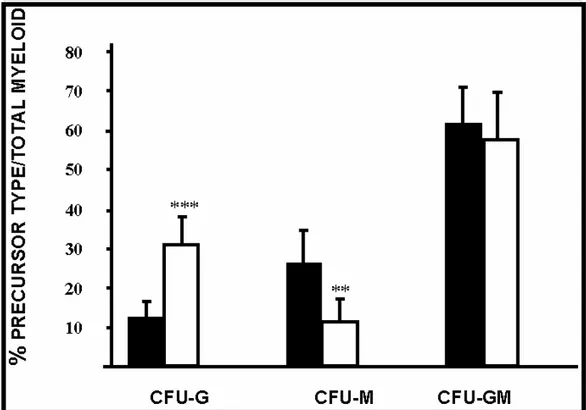
Il secondo passo è stato quello di considerare singolarmente le varie sottopopolazioni rispetto al numero totale di precursori mieloidi. Mentre la frazione delle colonie GM resta pressoché invariata nei due gruppi di topi, nei topi
Otx1-/- ho osservato un significativo aumento dei precursori unipotenti dei
granulociti ed una concomitante diminuzione dei precursori unipotenti dei macrofagi rispetto ai wild type (Fig.4.2). Nel complesso queste osservazioni suggeriscono che l’inattivazione di Otx1 induce un’alterazione della differenziazione mielo-monocitaria in particolare a livello del commitment dei precursori dei granulociti o dei macrofagi, con uno sbilanciamento a favore della granulopoiesi.
b) 7 mesi a) 1 mese
Figura 4.1 Precursori mieloidi totali (CFU-GM + CFU-G + CFU-M) a 1 mese (a), e a 7 mesi di vita (b) di topi wild type (nero) e Otx1-/-(bianco).
Analisi condotta mediante saggi clonogenici in colture di metilcellulosa, (media + d.s., * p<0.05; test di Student, coda=2, tipo=3)
Figura 4.2 Singoli precursori mieloidi rispetto al totale di topi wild type (nero) e Otx1-/- (bianco). Il midollo è stato piastrato su terreno semisolido e
4.2 EFFETTO DELL’ESPRESSIONE COSTITUTIVA DI Scl
NEI TOPI Otx1
-/-Nel nostro laboratorio abbiamo precedentemente dimostrato che l’inattivazione di Otx1determina un fenotipo anemico dovuto ad un difetto intrinseco delle cellule ematopoietiche piuttosto che ad anomalie nel microambiente circostante. Tuttavia tale anemia è del tutto recuperata quando nei knock-outs viene espresso in maniera costitutiva Scl, un master gene dell’ematopoiesi, che insieme a GATA-1 controlla la differenziazione del lineage eritroide. Tale studio è stato condotto su
topi doppi mutanti, Otx1-/-; pSil/Scl, che non esprimono Otx1 e nello stesso tempo
attivano la trascrizione di Scl a partire dal promotore Sil, Scl Interrupting Locus, costitutivamente attivo in cellule proliferanti. Infatti, saggi clonogenici condotti
sul midollo osseo di topi wild-type, Otx1-/- ed Otx1-/-; pSil/Scl dell’età di un mese
hanno permesso di osservare che nei doppi mutanti si verifica un recupero altamente significativo dell’eritropoiesi. Inoltre, l’analisi molecolare ha
evidenziato che nei topi Otx1-/-; pSil/Scl l’espressione di GATA-1, fortemente
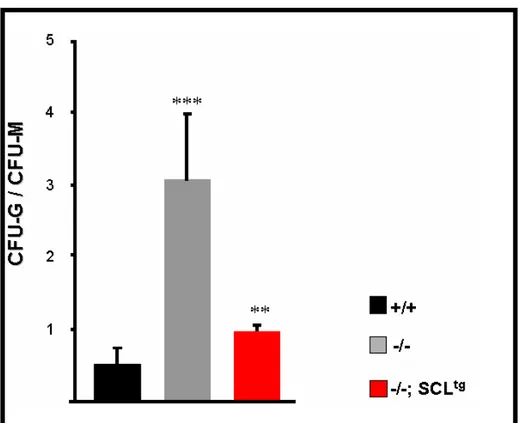
diminuita nei mutanti nulli, ritorna a livelli normali, indicando quindi che Otx1 opera attraverso Scl il controllo della differenziazione eritrocitaria (Levantini et al., 2003). Dal momento che Scl interviene nel regolare l’ematopoiesi a più livelli ho voluto verificare se Otx1 non adottasse lo stesso meccanismo d’azione anche nel regolare il lineage mielo-monocitario Come mostrato in Figura 4.3, nei wild type il rapporto fra CFU-G e CFU-M assume un valore inferiore a 1 ed è pertanto
a favore dei precursori macrofagici; al contrario, nei midolli Otx1-/-, questo
rapporto è fortemente sbilanciato a favore dei precursori granulocitari, mentre nei topi che esprimono Scl in maniera costitutiva il numero di CFU-G e CFU-M è pressoché paritario. L’insieme di questi dati indica che lo sbilanciamento
osservato nelle frequenze relative delle singole sottopopolazioni mieloidi nei topi
Otx1-/- non viene completamente recuperato dall’overespressione di Scl, quindi
Otx1 agisce nella regolazione del lineage mielo-monocitario attraverso un pathway alternativo o complementare a quello che utilizza nella regolazione dell’eritropoiesi.
Figura 4.3 Rapporto fra i precursori monopotenti dei
granulociti e quelli monopotenti dei macrofagi di topi wild type (nero), Otx1-/- (grigio), e doppi mutanti Otx1-/-;pSil/Scl (rosso).
Analisi condotta mediante saggi clonogenici in colture di metilcellulosa, (media + d.s., *** p<0.001; **p< 0.005; test di Student, coda=2, tipo=3)
4.3 ANALISI COMPARATIVA DELL’ESPRESSIONE DI
CANDIDATI TARGETS MOLECOLARI DI Otx1 IN MIDOLLI
WILD TYPE E Otx1
-/-La questione successiva che mi sono posta ha riguardato quindi l’identificazione di altri candidati geni targets di Otx1 nel controllo della mielopoiesi. A tale proposito, ho preso in esame due importanti regolatori della differenziazione
mielo-monocitaria: il gene PU.1 e il gene C/EBPα. PU.1 codifica un fattore di
trascrizione attivo nei tessuti ematopoietici (milza, timo e midollo), ed è espresso a livelli significativi nei precursori dei monociti/macrofagi e nei linfociti B (Tenen et al., 1997; Fisher et al., 1998) Inoltre, nella regione regolatrice che controlla la trascrizione di PU.1 è presente un sito bicoid, sequenza che può essere riconosciuta e legata in maniera specifica dall’omeodominio di Otx1.
C/EBPα è anch’esso un fattore di trascrizione espresso ad alti livelli nelle cellule
mielo-monocitiche, che interviene subito dopo l’induzione della differenziazione mentre viene down-regolato con il procedere della maturazione (Tenen et al., 1997).
Nell’analisi da me svolta, ho innanzitutto confrontato l’espressione dei geni PU.1
e C/EBPα nel midollo osseo di topi a 1 mese di vita, in due coppie di animali wild
type e di mutanti Otx1-/-. In particolare, dalle cellule midollari prelevate dai
femori, ho estratto l’RNA totale e dopo averlo retrotrascritto ho amplificato il cDNA mediante PCR semiquantitativa. Il gene costitutivo che mi ha consentito di fare questo confronto è stato Hprt. Infatti, dapprima ho considerato varie diluizioni (1:10; 1:100; 1:1000) dei diversi campioni di cDNA che ho poi amplificato con una coppia di primers specifica per Hprt. Confrontando la resa delle amplificazioni, ho potuto così identificare, per i diversi campioni, le
diluizioni contenenti la stessa quantità di cDNA, sulle quali ho eseguito lo studio dell’espressione dei geni candidati. Dalla Fig. 4.4 risulta infatti chiaro che il segnale del gene costitutivo è paragonabile nei wild type rispetto ai knock-out. Pertanto, le variazioni riscontrabili nella quantità dell’RNA dei geni candidati dei
topi Otx1-/- non è dovuta ad una diversa quantità di cDNA utilizzato, ma piuttosto
è compatibile con l’idea che sia un effetto dell’assenza di Otx1. Il controllo negativo che mi ha permesso di escludere la presenza di contaminazioni è
rappresentato dalla PCR eseguita sull’H2O utilizzata nella retrotrascrizione.
Per quanto riguarda il midollo osseo i risultati (Fig. 4.4), indicano che
l’espressione di PU.1, nel midollo dei topi Otx1-/-, appare diminuita rispetto a
quella riscontrata nei wild type mentre l’espressione di C/EBPα in una coppia
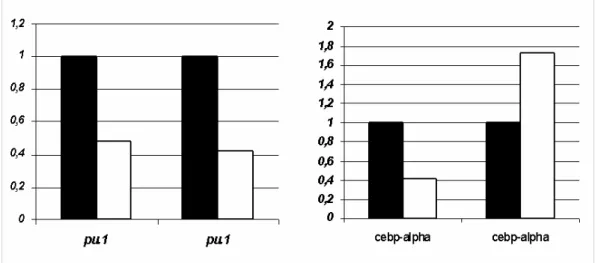
diminuisce mentre nell’altra aumenta. Ho successivamente effettuato l’analisi densitometrica delle bande ottenute (attraverso il programma Scion Image) che mi ha permesso di quantificare una diminuzione pari circa al 60% dell’espressione di PU.1 nei midolli knock-out rispetto ai wild type (Fig.4.5).
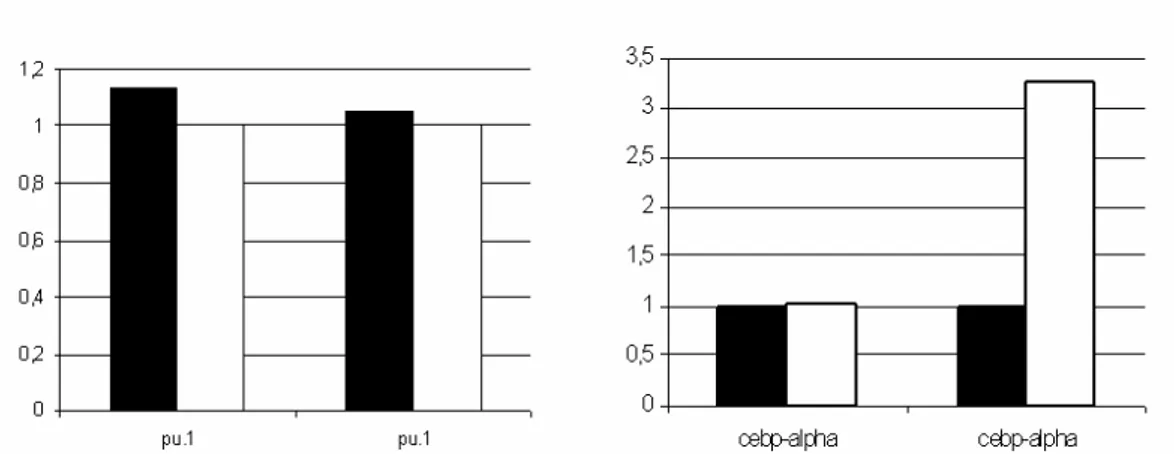
Ho infine preso in esame l’espressione degli stessi geni in pools di colonie di tipo GM, in quanto sono costituite solo da cellule del lineage mielo-monocitario. Colonie GM, ottenute attraverso saggi clonogenici, sono state prelevate al giorno 7 fino ad ottenere dei pools di 500.000-2.500.000 cellule. Data l’esiguità del materiale, ho cercato di purificare il più possibile estraendo da queste cellule l’mRNA. Per il resto ho condotto l’analisi molecolare come già precedentemente descritto per i midolli. L’analisi dell’espressione degli stessi geni non ha evidenziato particolari variazioni in entrambe le coppie di topi: infatti
l’espressione di PU.1 diminuisce leggermente e quella di C/EBPα in un caso
(Fig4.6); anche questo dato è stato quantificato tramite analisi densitometrica (Fig.4.7).
Nel complesso l’insieme dei dati raccolti rivela che Otx1, oltre a controllare l’eritropoiesi, agisce anche nella regolazione della differenziazione dei lineages mielo-monocitari, la sua inattivazione è infatti associata ad un’incremento della granulopoiesi e ad una concomitante diminuzione del lineage monocitario e il suo meccanismo d’azione sembra dipendere solo parzialmente da Scl. Otx1, verosimilmente esercita un’azione di controllo a livello del commitment dei progenitori bipotenti interagendo direttamente o indirettamente con PU.1, importante regolatore della mielopoiesi.
Figura 4.4 Confronto dei livelli di espressione di PU.1 e C/EBPα in due coppie di midolli wild type e Otx1-/- tramite RT-PCR semiquantitativa. HPRT è stato utilizzato come controllo costitutivo.
Figura 4.5 Analisi densitometrica delle bande ottenute in Figura 4.4. Wild type (nero) e Otx1-/- (bianco), (programma Scion Image).
Figura 4.6 Confronto dei livelli di espressione di PU.1 e C/EBPα in pools di colonie CFU-GM wild type e Otx1-/- tramite RT-PCR semiquantitativa. HPRT è stato utilizzato come controllo costitutivo.
Figura 4.7 Analisi densitometrica delle bande ottenute in Figura 4.6. Wild type (nero) e Otx1-/- (bianco), (programma Scion Image).