3 RISULTATI
3.1 ISOLAMENTO ED IDENTIFICAZIONE DEI CEPPI DI
LIEVITO
Nel periodo compreso tra agosto 2010 e aprile 2011 sono stati isolati
e successivamente identificati 163 ceppi di lievito da campioni biologici di
varia natura, pervenuti all’Unità Operativa di Microbiologia, presso l’Azienda
Ospedaliera Universitaria Pisana.
In particolare, i ceppi utilizzati in questo studio provenivano da
pazienti ricoverati nei seguenti reparti: centro ustioni, medicina generale,
ambulatorio del piede diabetico e pneumologia endoscopica ambulatoriale.
Tabella 5 : Caratteristiche dei ceppi isolati ed identificati in questo studio di tesi
Suscettibiltà agli antifungini (MIC, µg/ml)
Paziente Specie Distretto di
isolamento
Reparto ANDa MFa CASa FCb PZd VORd IZd FZd ABc
CP 1 C. albicans URINE g CUS i 0,12 0,008 0,06 0,08 0,06 0,008 0,12 0,5 0,25
CP 2 C. albicans ESP. e MED4 l 0,06 0,008 0,12 0,06 0,06 0,06 0,12 0,12 0,25
CP 3 C. albicans BAL. e PNEND 0,06 0,008 0,03 0,06 0,015 0,008 0,06 0,5 0,5
CP 4 C. albicans URINE 5MED l 0,12 0,015 0,12 0,06 0,03 0,008 0,12 0,5 0,5
CP 5 C. albicans T. CUT. f PIEDI m 0,03 0,008 0,03 0,06 0,015 0,008 0,06 0,5 0,5
CP 6 C. albicans T. CUT. PIEDI 0,03 0,008 0,03 0,06 0,008 0,008 0,015 0,5 0,25
CP 7 C. albicans ESP. 5MED ND * ND ND ND ND ND 0,032 1 ND
CP 8 C. albicans BAL. PNEND n 0,03 0,03 0,03 0,06 0,015 0,008 0,06 0,25 0,5
CP 9 C. albicans CATETERE g MED4 0,12 0,015 0,12 0,06 0,03 0,008 0,06 0,25 0,5
CP 10 C. albicans B. ASP. e 5MED 0,06 0,015 0,12 2 0,06 0,008 0,12 0,25 0,5
CP 11 C. albicans URINE MED4 0,12 0,015 0,25 0,12 0,03 0,008 0,12 0,25 0,25
CP 12 C. albicans ESP. MED4 ND ND ND ND ND 0,016 0,023 0,125 ND
CP 13 C. albicans URINE 5MED 0,12 0,015 0,12 0,06 0,06 0,008 0,12 0,5 0,5
CP 14 C. albicans ESP. MED4 0,03 0,015 0,03 0,06 0,06 0,008 0,06 0,25 0,5
CP 15 C. albicans ESP. 5MED 0,015 0,015 0,03 0,06 0,06 0,008 0,06 0,12 0,5
CP 16 C. albicans URINE MED4 0,12 0,015 0,06 0,12 0,015 0,008 0,06 0,25 0,5
CP 17 C. albicans ESP. 5MED 0,03 0,008 0,008 0,12 0,015 0,008 0,03 0,25 0,5
CP 18 C. albicans BAL. PNEND 0,12 0,008 0,06 0,06 0,03 0,008 0,06 0,25 0,5
CP 19 C. albicans URINE 5MED 0,03 0,008 0,06 0,06 0,015 0,008 0,015 0,25 0,5
CP 20 C. albicans BAL. PNEND 0,12 0,008 0,12 0,06 0,06 0,015 0,12 0,25 0,25
Suscettibiltà agli antifungini (MIC, µg/ml)
Paziente Specie Distretto di
isolamento
Reparto ANDa MFa CASa FCb PZd VORd IZd FZd ABc
CP 22 C. albicans BAL. PNEND 0,06 0,015 0,06 0,06 0,015 0,008 0,12 1 0,5
CP 23 C. albicans ESP. 5MED 0,12 0,015 0,25 0,06 0,03 0,015 0,12 0,5 0,25
CP 24 C. albicans ESP. 5MED 0,12 0,015 0,06 0,06 0,06 0,008 0,12 0,5 0,25
CP 25 C. albicans URINE 5MED 0,12 0,015 0,06 0,06 0,06 0,008 0,12 0,5 0,25
CP 26 C. albicans B. ASP. 5MED 0,03 0,015 0,12 0,06 0,03 0,008 0,06 0,5 0,25
CP 27 C. albicans ESP. MED4 0,03 0,015 0,06 0,06 0,03 0,008 0,06 0,25 ND
CP 28 C. albicans ESP. 5MED 0,12 0,015 0,12 0,06 0,06 0,008 0,12 0,25 0,5
CP 29 C. albicans T. CUT. PIEDI 0,06 0,008 0,06 0,06 0,03 0,015 0,06 0,5 0,5
CP 30 C. albicans ESP. MED4 0,015 0,008 0,06 0,06 0,03 0,015 0,12 1 0,5
CP 31 C. albicans URINE MED4 ND ND ND ND ND ND 0,012 0,19 ND
CP 32 C. albicans B. ASP. PNEND 0,06 0,008 0,06 0,06 0,015 0,008 0,06 0,25 0,5
CP 33 C. albicans B. ASP. CUS 0,03 0,015 0,03 0,06 0,06 0,008 0,12 0,5 0,5
CP 34 C. albicans URINE CUS 0,06 0,008 0,06 0,06 0,015 0,008 0,06 0,5 0,5
CP 35 C. albicans URINE MED4 0,06 0,008 0,06 0,06 0,015 0,008 0,06 0,5 0,5
CP 36 C. albicans B. ASP. 5MED 0,12 0,008 0,12 0,12 0,06 0,008 0,12 0,5 0,5
CP 37 C. albicans URINE MED4 0,12 0,015 0,25 0,06 0,06 0,008 0,12 0,25 0,5
CP 38 C. albicans URINE CUS 0,06 0,008 0,006 0,25 0,01 0,008 0,12 0,15 0,25
CP 39 C. albicans URINE MED4 ND ND ND ND ND ND 0,032 1 ND
CP 40 C. albicans URINE 5MED 0,015 0,015 0,12 0,06 0,06 0,015 0,12 0,25 0,25
CP 41 C. albicans ESP. 5MED 0,015 0,015 0,03 0,25 0,03 0,008 0,06 0,25 0,5
CP 42 C. albicans URINE CUS 0,015 0,008 0,12 0,06 0,06 0,008 0,06 0,25 0,5
CP 43 C. albicans URINE 5MED ND ND ND ND ND ND 0,023 0,38 ND
CP 44 C. albicans ESP. MED4 0,03 0,008 0,06 0,06 0,125 0,015 0,06 1 0,5
CP 45 C. albicans ESP. 5MED 0,12 0,008 0,06 0,06 0,03 0,008 0,06 0,5 0,5
Suscettibiltà agli antifungini (MIC, µg/ml)
Paziente Specie Distretto di
isolamento
Reparto ANDa MFa CASa FCb PZd VORd IZd FZd ABc
CP 47 C. albicans URINE MED4 0,06 0,015 0,12 0,06 0,06 0,008 0,12 0,5 0,5
CP 48 C. albicans ESP. MED4 0,06 0,015 0,06 0,06 0,03 0,015 0,06 1 1
CP 49 C. albicans B. ASP. 5MED 0,003 0,015 0,06 0,12 1 0,25 0,5 8 0,5
CP 50 C. albicans ESP. 5MED 0,015 0,008 0,03 0,06 0,015 0,015 0,06 1 0,25
CP 51 C. albicans ESP. 5MED 0,015 0,03 0,06 0,12 0,06 0,015 0,12 0,5 0,5
CP 52 C. albicans ESP. MED4 0,12 0,015 0,12 0,06 0,06 0,008 0,06 0,5 0,5
CP 53 C. albicans BAL. PNEND 0,06 0,006 0,06 0,06 0,015 0,008 0,06 0,5 0,5
CP 54 C. albicans URINE MED4 0,06 0,008 0,06 0,06 0,03 0,008 0,06 0,25 0,25
CP 55 C. albicans EMO. h CUS 0,03 0,008 0,08 0,06 0,015 0,008 0,06 0,25 0,5
CP 56 C. albicans T. FAR e. CUS 0,06 0,008 0,12 0,06 0,01 0,008 0,06 0,25 0,25
CP 57 C. albicans B. ASP. 5MED 0,12 0,008 0,25 0,06 0,06 0,008 0,12 0,25 0,5
CP 58 C. albicans BAL. PNEND 0,12 0,008 0,12 0,06 0,03 0,008 0,12 0,25 0,5
CP 59 C. albicans URINE MED4 0,12 0,015 0,03 0,06 0,06 0,008 0,12 0,5 0,5
CP 60 C. albicans URINE CUS 0,03 0,008 0,06 0,12 0,015 0,008 0,06 0,5 0,5
CP 61 C. albicans URINE 5MED 0,015 0,008 0,08 0,12 0,015 0,008 0,015 0,5 0,5
CP 62 C. albicans BAL. PNEND 0,03 0,008 0,06 0,12 0,015 0,008 0,03 0,5 0,5
CP 63 C. albicans ESP. MED4 0,06 0,008 0,06 0,06 0,03 0,008 0,06 0,5 0,5
CP 64 C. albicans B. ASP. CUS 0,03 0,125 0,25 4 0,5 0,25 0,25 32 0,5
CP 65 C. albicans URINE 5MED 0,12 0,015 0,12 0,06 0,06 0,008 0,12 0,5 0,5
CP 66 C. albicans B. ASP. 5MED 0,006 0,015 0,12 0,06 0,06 0,008 0,12 0,5 0,25
CP 67 C. albicans URINE 5MED 0,25 0,015 0,25 0,06 0,06 0,008 0,12 0,5 0,5
CP 68 C. albicans ESP. MED4 0,015 0,008 0,06 0,06 0,008 0,008 0,03 0,12 0,5
CP 69 C. albicans URINE CUS 0,06 0,008 0,06 0,06 0,015 0,008 0,03 0,25 0,5
CP 70 C. albicans BAL. PNEND 0,03 0,015 0,06 0,5 0,03 0,015 0,06 0,5 0,5
Suscettibiltà agli antifungini (MIC, µg/ml)
Paziente Specie Distretto di
isolamento
Reparto ANDa MFa CASa FCb PZd VORd IZd FZd ABc
CP 72 C. albicans B. ASP. CUS 0,015 0,008 0,03 0,06 0,03 0,008 0,06 0,25 0,25
CP 73 C. albicans URINE MED4 0,12 0,016 0,12 0,06 0,06 0,008 0,06 0,25 0,5
CP 74 C. albicans BAL. PNEND 0,015 0,008 0,06 0,06 0,015 0,008 0,03 0,5 0,5
CP 75 C. albicans BAL. PNEND ND ND ND ND ND ND 0,047 0,75 ND
CP 76 C. albicans URINE CUS 0,03 0,008 0,06 0,06 0,06 0,008 0,12 0,5 0,25
CP 77 C. albicans B. ASP. CUS 0,12 0,008 0,06 0,06 0,06 0,015 0,12 0,5 0,25
CP 78 C. albicans URINE 5MED 0,06 0,03 0,06 1 0,03 0,008 0,06 0,12 0,5
CP 79 C. albicans BAL. PNEND 0,06 0,015 0,06 0,06 0,03 0,015 0,06 1 0,5
CP 80 C. albicans URINE 5MED 0,06 0,03 0,08 0,12 0,015 0,008 0,06 0,5 0,5
CP 81 C. albicans BAL. PNEND 0,12 0,015 0,08 1 0,03 0,015 0,06 0,5 0,5
CP 82 C. albicans B. ASP. 5MED 0,06 0,008 0,06 0,06 0,06 0,008 0,12 0,5 0,5
CP 83 C. albicans B. ASP. 5MED 0,015 0,008 0,03 0,06 0,06 0,015 0,12 1 0,25
CP 84 C. albicans URINE MED4 0,015 0,008 0,03 0,06 0,03 0,015 0,12 0,5 0,5
CP 85 C. albicans T. FAR. CUS 0,12 0,008 0,25 0,06 0,03 0,008 0,12 0,25 0,5
CP 86 C. albicans T. FAR. CUS 0,018 0,008 0,03 0,06 0,03 0,008 0,12 0,25 0,25
CP 87 C. albicans URINE CUS 0,015 0,015 0,03 0,5 0,06 0,008 0,12 0,5 0,25
CP 88 C. albicans URINE MED4 0,12 0,008 0,12 0,06 0,06 0,015 0,12 1 0,25
CP 89 C. albicans BAL. MED4 0,12 0,015 0,25 0,06 0,06 0,008 0,12 0,25 0,5
CP 90 C. albicans ESP. MED4 0,12 0,015 0,12 0,06 0,06 0,008 0,06 0,12 0,25
CP 91 C. albicans B. ASP. PNEND 0,015 0,015 0,06 0,06 0,015 0,008 0,06 0,5 0,5
CP 92 C. albicans B. ASP. PNEND 0,12 0,015 0,25 0,5 8 8 16 64 0,5
CP 93 C. albicans B. ASP. CUS 0,12 0,015 0,12 0,12 0,015 0,008 0,06 0,5 0,5
CP 94 C. albicans URINE MED4 0,12 0,015 0,06 0,12 0,25 0,015 0,25 1 0,25
CP 95 C. albicans B. ASP. CUS 0,12 0,015 0,12 0,06 0,06 0,008 0,06 0,25 0,25
Suscettibiltà agli antifungini (MIC, µg/ml)
Paziente Specie Distretto di
isolamento
Reparto ANDa MFa CASa FCb PZd VORd IZd FZd ABc
CP 97 C. albicans B. ASP. CUS 0,12 0,015 0,06 0,06 0,015 0,008 0,015 0,5 0,25
CP 98 C. parapsilosis EMO MED4 2,00 1,00 0,5 0,06 0,06 0,008 0,12 0,25 0,25
CP 99 C. parapsilosis B. ASP. PNEND 1 4 1 0,06 0,06 0,06 0,12 0,5 0,5
CP 100 C. parapsilosis T. CUT. PIEDI 1 2 0,5 0,25 0,06 0,03 0,12 1 0,5
CP 101 C. parapsilosis BAL PNEND 2 2 1 0,06 0,06 0,008 0,12 0,25 0,5
CP 102 C. parapsilosis T. CUT. PIEDI 1 1 0,5 0,12 0,03 0,015 0,12 1 0,5
CP 103 C. parapsilosis BAL PNEND 2 2 0,5 0,12 0,06 0,03 0,12 1 0,5
CP 104 C. parapsilosis B. ASP. PNEND 1,00 2,00 1 0,12 0,06 0,015 0,12 1 0,5
CP 105 C. parapsilosis T. CUT. PIEDI 2 2 0,25 0,12 0,06 0,015 0,06 1 0,5
CP 106 C. parapsilosis B. ASP. PNEND 2 2 1 0,06 0,03 0,008 0,12 0,25 0,25
CP 107 C. parapsilosis B. ASP. PNEND 1 1 0,25 0,12 0,06 0,008 0,12 0,5 0,5
CP 108 C. parapsilosis B. ASP. PNEND 1 2 0,5 0,12 0,03 0,015 0,12 1 0,5
CP 109 C. parapsilosis BAL PNEND 1 1 0,5 0,12 0,06 0,03 0,12 1 0,5
CP 110 C. parapsilosis BAL. CUS 1,00 1,00 0,5 2 0,06 0,008 0,12 0,5 0,5
CP 111 C. parapsilosis T. CUT. PIEDI 1,00 2,00 1 0,06 0,125 0,008 0,25 0,25 0,25
CP 112 C. parapsilosis T. CUT. PIEDI 2 2 0,5 0,06 0,03 0,015 0,12 1 0,5
CP 113 C. parapsilosis B. ASP. PNEND 2,00 2,00 0,5 0,12 0,06 0,015 0,06 1 0,5
CP 114 C. parapsilosis T. CUT. PIEDI ND ND ND ND ND 0,023 0,38 0,19 ND
CP 115 C. parapsilosis B. ASP. PNEND 2,00 2,00 1 0,25 0,125 0,008 0,12 0,25 1
CP 116 C. parapsilosis T. CUT. PIEDI 2,00 2,00 0,8 0,125 0,015 0,25 1 1 0,5
CP 117 C. parapsilosis B. ASP. PNEND 1 1 0,5 0,12 0,06 0,03 0,12 1 0,5
CP 118 C. parapsilosis BAL. PNEND 1 1 0,25 0,06 0,06 0,008 0,12 0,5 0,5
CP 119 C. parapsilosis EMO. CUS 2,00 2,00 0,5 0,12 0,06 0,015 0,12 0,5 0,25
CP 120 C. parapsilosis EMO. CUS 2,00 2,00 1 0,06 0,06 0,008 0,12 1 0,25
Suscettibiltà agli antifungini (MIC, µg/ml)
Paziente Specie Distretto di
isolamento
Reparto ANDa MFa CASa FCb PZd VORd IZd FZd ABc
CP 122 C. parapsilosis EMO. CUS 2,00 1,00 0,5 0,06 0,06 0,008 0,12 0,5 0,25
CP 123 C. tropicalis URINE MED4 0,12 0,015 0,06 0,06 0,06 0,008 0,12 0,5 0,5
CP 124 C. tropicalis URINE MED4 0,5 0,06 0,25 0,06 0,125 0,12 0,25 2 0,5
CP 125 C. tropicalis B. ASP. MED4 0,06 0,03 0,06 0,06 0,125 0,06 0,25 1 1
CP 126 C. tropicalis B. ASP. CUS 0,12 0,060 0,12 0,06 0,125 0,030 0,12 0,5 0,5
CP 127 C. tropicalis B. ASP. 5MED 0,12 0,06 0,06 0,25 0,5 0,25 0,5 2 1
CP 128 C. tropicalis ESP. 5MED 0,12 0,06 0,03 0,06 0,125 0,03 0,12 0,5 1
CP 129 C. tropicalis EMO. MED4 0,06 0,015 0,03 0,06 0,125 0,03 0,25 1 1
CP 130 C. tropicalis URINE 5MED 0,12 0,03 0,06 0,06 0,125 0,015 0,25 0,25 1
CP 131 C. tropicalis B. ASP. CUS 0,12 0,03 0,06 64 0,25 0,06 0,25 1 0,5
CP 132 C. tropicalis BAL. PNEND 0,03 0,03 0,06 64 0,25 0,12 0,25 4 1
CP 133 C. tropicalis URINE CUS 0,12 0,06 0,25 0,06 0,125 0,03 0,25 0,5 1
CP 134 C. krusei B. ASP. CUS 0,03 0,125 0,25 4 0,25 0,120 0,25 16 0,5
CP 135 C. krusei BAL. PNEND 0,03 0,050 0,12 4 0,25 0,120 0,25 32 0,5
CP 136 C. krusei EMO. MED4 0,12 0,125 0,5 16 0,5 0,500 0,5 32 0,5
CP 137 C. krusei ESP. 5MED 0,06 0,125 0,25 8 0,25 0,250 0,5 64 1
CP 138 C. krusei MAT. VARIO g MED4 0,25 0,125 0,06 8 0,5 0,500 2 64 1
CP 139 C. kefyr B. ASP. 5MED 0,12 0,06 0,06 0,12 0,06 0,008 0,12 0,12 1
CP 140 C. kefyr T. CUT. CUS 0,12 0,03 0,03 0,06 0,125 0,015 0,12 0,5 2
CP 141 C. kefyr URINE CUS 0,12 0,06 0,015 0,5 0,06 0,008 0,12 0,12 1
CP 142 C. kefyr URINE CUS 0,12 0,05 0,06 1 0,125 0,008 0,12 0,25 1
CP 143 C. famata ESP. MED4 0,03 0,015 0,06 0,06 0,03 0,008 0,06 0,25 ND
CP 144 C. famata URINE MED4 1 0,500 0,5 0,06 0,06 0,015 0,12 0,5 0,25
CP 145 C. famata B. ASP. PNEND 0,5 0,500 0,25 0,12 0,06 0,030 0,12 1 0,25
Suscettibiltà agli antifungini (MIC, µg/ml)
Paziente Specie Distretto di
isolamento
Reparto ANDa MFa CASa FCb PZd VORd IZd FZd ABc
CP 147 C. guilliermondii B. ASP. PNEND 2 2,000 8 0,06 0,5 0,120 1 8 0,25
CP 148 C. glabrata ESP. 5MED 0,03 0,01 0,25 0,06 1 2 1 32 1
CP 149 C. glabrata ESP. 5MED 0,12 0,008 0,12 0,06 0,06 0,008 0,12 0,5 0,25
CP 150 C. glabrata T. VAGINALE f 5MED 0,015 0,015 0,06 0,06 0,5 0,12 0,5 4 0,5
CP 151 C. glabrata B. ASP. CUS 0,12 0,008 0,06 0,06 0,06 0,008 0,12 0,5 0,5
CP 152 C. glabrata B. ASP. MED4 0,03 0,015 0,12 0,06 1 0,25 0,5 8 0,5
CP 153 C. glabrata B. ASP. PNEND 0,03 0,008 0,12 0,06 8 4 16 256 0,25
CP 154 C. glabrata B. ASP. PNEND 0,015 0,015 0,06 0,06 1 0,25 0,5 8 0,5
CP 155 C. dubliniensis ESP. 5MED 0,12 0,03 0,25 0,06 0,03 0,008 0,06 0,12 0,25
CP 156 C. dubliniensis B. ASP. CUS 0,25 0,06 0,25 0,06 0,03 0,008 0,06 0,12 0,25
CP 157 C. dubliniensis B. ASP. CUS 0,12 0,06 0,25 0,06 0,015 0,008 0,015 0,12 0,25
CP 158 C. dubliniensis B. ASP. CUS 0,06 0,03 0,08 0,06 0,06 0,008 0,06 0,25 0,25
CP 159 S. cerevisiae B. ASP. CUS 0,25 0,125 0,25 0,06 0,25 0,06 0,25 4 0,5
CP 160 S. cerevisiae BAL. PNEND 0,12 1 0,25 0,06 0,25 0,06 0,25 4 0,5
CP 161 C. utilis B. ASP. PNEND 0,015 0,015 0,03 0,06 0,25 0,12 0,25 4 0,5
CP 162 C. haemulonii T. CUT. PIEDI 0,06 0,06 0,03 0,06 0,02 0,03 0,12 2,00 1
CP 163 C. sphaerica ESP. MED4 0,03 0,015 0,12 0,12 0,50 0,50 1,00 32,00 0,50
a
AND=anidulafungina, CAS=caspofungina, MICA=micafungina
b
FC=5-fluorocitosina
c
AB=amfotericina B
d
POS=posaconazolo, FZ=fluconazolo, IZ=itraconazolo, VOR=voriconazolo e
f
T.CUT.=tampone cutaneo, T.vaginale=tampone vaginale g
MAT.VARIO=materiale vario h
EMO=emocolture i
CUS=reparto centro ustioni di AOUP (Azienda Ospedaliera Universitaria Pisana) l
MED4/5MED=reparto medicina generale di AOUP m
PIEDI=ambulatorio piede diabetico di AOUP n
PNEND=reparto pneumologia ambulatoriale endoscopica di AOUP
*
Risultati, 63
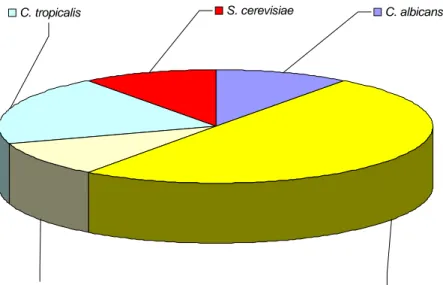
Come riportato in Figura 18, le specie isolate dai pazienti,
provenienti dal reparto centro ustioni appartenevano prevalentemente al
genere Candida, con C. albicans la specie di maggiore frequenza (54%),
seguita da C. parapsilosis (11%). Le specie C. tropicalis, C. kefyr e C.
dubliniensis sono state isolate con la stessa frequenza (9%), C. krusei e C.
glabrata e il lievito Saccaromyces cerevisiae sono risultate caratterizzate
da una più bassa percentuale di isolamento (3%).
Figura 18.
Distribuzione delle principali specie di lievito isolate da pazienti del centro ustioni (numero totale=35). Con n° è indicato il numero dei ceppi di lievito e con f la frequenza di isolamento.C. albicans C. parapsilosis C. krusei C. tropicalis S. cerevisiae C. dubliniensis C. glabrata C. kefyr C. albicans (n°=19; f=54%) C. parapsilosis (n°=4; f=11%) C. krusei (n°=1; f=3%) C. tropicalis (n°=3; f=9%) C. kefyr (n°=3; f=9%) C. glabrata (n°=1; f=3%) C. dubliniensis (n°=3; f=9%) S. cerevisiae (n°=1; f=3%)
Risultati, 64
In Figura 19, sono illustrati i dati relativi ai ceppi provenienti dai
reparti di medicina generale, tutti identificati come specie del genere
Candida: C. albicans è risultata la specie maggiormente isolata (73%),
seguita da C. tropicalis (7%), C. glabrata (5%), C. krusei (4%), C.
parapsilosis (3%), C. famata (3%) e C. kefyr, C. dubliniensis e C. sphaerica
di più raro isolamento (1%).
Figura 19.
Distribuzione delle principali specie di lievito isolate da pazientidi medicina generale (numero totale=79). Con n° è indicato il numero dei ceppi di lievito e con f la frequenza di isolamento.
C. parapsilosis C. krusei C. tropicalis C. kefyr C. famata C. glabrata C. albicans C. sphaerica C. dubliniensis C. albicans (n°=58;f=73%) C. parapsilosis (n°=2; f=3%) C. krusei (n°=3; f=4%) C. tropicalis (n°=7; f=9%) C. kefyr (n°=1; f =1%) C. famata (n°=2; f=3%) C. glabrata (n°=4; f=5%) C. dubliniensis (n°=1; f=1%) C. sphaerica (n°=1; f=1%)
Risultati, 65
Per quanto concerne i campioni isolati da pazienti afferenti
all’ambulatorio del piede diabetico, come è possibile osservare in Figura
20, C. parapsilosis è risultata la specie di maggiore prevalenza tra le specie
appartenenti al genere Candida con una frequenza pari al 64%, seguita da
C. albicans (27%) ed, in percentuale inferiore, è stata isolata C. haemulonii
(9%).
Figura 20.
Distribuzione delle principali specie di lievito isolate da pazientidell’ambulatorio piede diabetico (numero totale=11). Con n° è stato indicato il numero dei ceppi di lievito e con f la frequenza di isolamento.
C. parapsilosis
C. albicans C. haemulonii
C. albicans (n°=3; f=27%) C. parapsilosis (n°=7; f=64%)
Risultati, 66
Infine, in Figura 21, sono riportati i dati relativi alle specie isolate dai
pazienti provenienti dal reparto di pneumologia ambulatoriale endoscopica.
Anche in questo caso, la maggior parte delle specie appartenevano al
genere Candida, con C. albicans isolata con una frequenza del 45%, a
seguire C. parapsilosis (32%), C. guilliermondii e C. glabrata (5%), mentre
C. tropicalis, C. krusei, C. utilis e il lievito S. cerevisiae sono state isolate
con minor frequenza (3%).
Figura 21.
Distribuzione delle principali specie di lievito isolate da pazientidel reparto di pneumologia ambulatoriale endoscopica (numero totale=38). Con n° è indicato il numero dei ceppi e con f la frequenza di isolamento.
C. parapsilosis C. krusei
C. tropicalis
C. famata C. guilliermondii C. glabrata
S. cerevisiae C. utilis C. albicans C. albicans (n°=17; f=45%) C. parapsilosis (n°=12; f=32%) C. krusei (n°=1; f=3%) C. tropicalis (n°=1; f=3%) C. famata (n°=1; f=3%) C. guilliermondii (n°=2; f=5%) C. glabrata (n°=2; f=5%) S. cerevisiae (n°=1; f=3%) C. utilis (n°=1; f=3%)
Risultati, 67
3.1.1
Distribuzione dei principali ceppi di lievito nei
reparti esaminati.
Il test esatto di Fischer a due code è stato impiegato per valutare la
diversa distribuzione delle 5 specie di Candida, più frequentemente isolate
in ambito nosocomiale (C. albicans, C. parapsilosis, C. glabrata, C.
tropicalis, C. krusei) nei 5 reparti inclusi nello studio. Mentre C. glabrata, C.
tropicalis, C. krusei non sono risultate associate ad un’elevata frequenza di
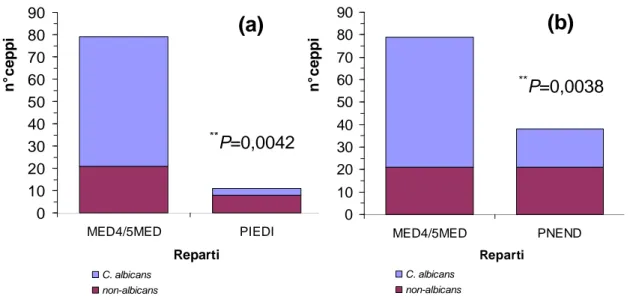
isolamento in nessuno dei reparti considerati, la specie C. albicans è
risultata isolata con maggiore frequenza nel reparto di medicina generale,
rispetto alla frequenza osservata tra i campioni provenienti dall’ambulatorio
piede diabetico (P=0,0042) e pneumologia ambulatoriale endoscopica
(P=0,0038) (Figura 22).
0 10 20 30 40 50 60 70 80 90 MED4/5MED PIEDI Reparti C. albicans non-albicans 0 10 20 30 40 50 60 70 80 90 MED4/5MED PNEND Reparti C. albicans non-albicansFigura 22.
Confronto tra la distribuzione della specie C. albicans tra icampioni provenienti dai reparti di medicina generale e ambulatorio piede diabetico (a) e medicina generale e pneumologia ambulatoriale endoscopica (b). Valori di P≤0,05 indicano una differenza statisticamente significativa.
**
P=0,0042
**P=0,0038
(a)
n ° c e p p i(b)
n ° c e p p iRisultati, 68
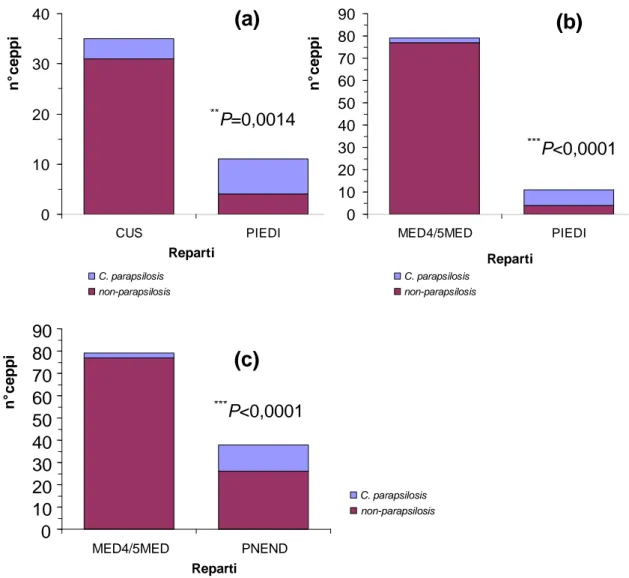
Al contrario per C. parapsilosis è stata osservata una maggiore frequenza di
isolamento, rispetto alle altre specie del genere Candida, nei campioni
provenienti dall’ambulatorio piede diabetico, rispetto a quelli isolati da
pazienti ricoverati presso il centro ustioni (P=0,0014) e presso i reparti di
medicina generale, rispetto a quelli dell’ambulatorio piede diabetico
(P<0,0001) e di pneumologia ambulatoriale endoscopica (P<0,0001)
(Figura 23).
0 10 20 30 40 CUS PIEDI Reparti C. parapsilosis non-parapsilosis 0 10 20 30 40 50 60 70 80 90 MED4/5MED PIEDI Reparti C. parapsilosis non-parapsilosisFigura 23. Confronto tra la distribuzione della specie C. parapsilosis nei reparti centro
ustioni e ambulatorio piede diabetico (a), in medicina generale e ambulatorio piede diabetico (b), in medicina generale e pneumologia ambulatoriale endoscopica (c). Valori di P≤0,05 indicano una differenza statisticamente significativa.
C. parapsilosis non-parapsilosis
0
10
20
30
40
50
60
70
80
90
MED4/5MED PNEND Reparti **P=0,0014
***P<0,0001
***P<0,0001
(a)
(b)
(c)
n ° c e p p i n ° c e p p i n ° c e p p iRisultati, 69
3.2 FREQUENZA DI ISOLAMENTO DEI CEPPI DI LIEVITO
IN DIVERSI CAMPIONI BIOLOGICI
Al fine di conoscere la frequenza di isolamento delle varie specie di
lievito nei differenti distretti anatomici sede di prelievo, i campioni pervenuti
al laboratorio sono stati suddivisi in 4 classi: campioni respiratori
(espettorati, tamponi faringei, bronco aspirati, lavaggi bronchiolo-alveolari),
emocolture, campioni polimicrobici (tamponi cutanei, tamponi vaginali,
tamponi anali), altri campioni (materiali vari, cateteri, urine).
Per quanto concerne il distretto respiratorio, Candida albicans é
risultata la specie maggiormente prevalente (58%), seguita da C.
parapsilosis (14%), C. tropicalis (7%), C. glabrata (6%), C. dubliniensis
(4%), C. krusei (3%) C. guilliermondii (2%) e C. famata (2%). Anche il lievito
Saccaromyces cerevisiae è stato isolato con una frequenza del 2%, mentre
C. famata, C. kefyr, C. utilis, C. sphaerica sono state identificate solamente
Risultati, 70
Figura 24.
Distribuzione delle principali specie di lievito isolate da campionirespiratori (tamponi faringei, lavaggi bronchiolo-alveolare, bronco aspirati, espettorati). Con n° è stato indicato il numero dei ceppi di lievito e con f la frequenza di isolamento. Numero totale=110
C. tropicalis C. krusei C. parapsilosis C. kefyr C. famata C. guilliermondii C. sphaerica C. albicans C. utilis S. cerevisiae C. dubliniensis C. glabrata C. albicans (n°=64; f=58%) C. parapsilosis (n°=16; f=15%) C. krusei (n°=3; f=3%) C. tropicalis (n°=7; f=6%) C. kefyr (n°=1; f=1%) C. famata (n°=2; f=2%) C. guilliermondii (n°=2; f=2%) C. glabrata (n°=7; f=6%) C. dubliniensis (n°=4; f=4%) S. cerevisiae (n°=2; f=2%) C. utilis (n°=1; f=1%) C. sphaerica (n°=1; f=1%)
Risultati, 71
Come riportato in Figura 25, invece, i ceppi di lievito isolati da
emocolture sono risultati appartenere prevalentemente alla specie C.
parapsilosis (50%), seguita da C. tropicalis (20%), mentre C. albicans, C.
krusei e il lievito S. cerevisiae sono stati isolati solamente nel 10% dei casi.
Figura 25.
Distribuzione delle principali specie di lievito isolate da emocolture. Con n° è stato indicato il numero dei ceppi di lievito e con f la frequenza di isolamento. Numero totale=10.C. tropicalis S. cerevisiae C. albicans
C. krusei
C. parapsilosis
C. albicans (n°=1; f=10%) C. parapsilosis (n°=5; f=50%)
C. krusei (n°=1; f=10%) C. tropicalis (n°=2; f=20%)
Risultati, 72
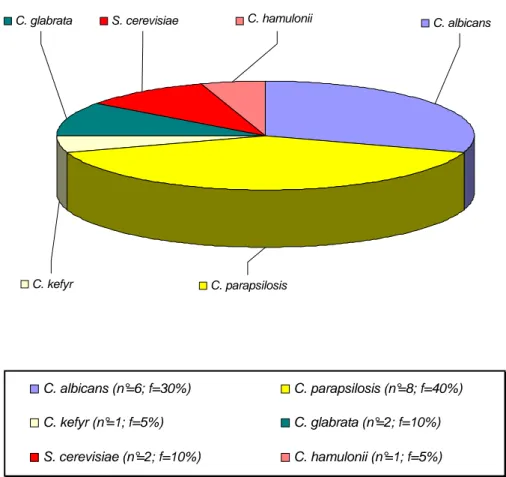
Nei tamponi prelevati da varie sedi corporee, la specie isolata con
maggiore frequenza è risultata C. parapsilosis (40%), seguita da C.
albicans, riscontrata con una percentuale del 30% e da C. glabrata e S.
cerevisae (10%). C. haemulonii e C. kefyr sono risultate specie di più raro
isolamento (5%) ( Figura 26).
Figura 26.
Distribuzione delle principali specie di lievito, isolate da vari tamponi (tamponi vaginali, cutanei, nasali, auricolari, anali). Con n° è stato indicato il numero dei ceppi di lievito e con f la frequenza di isolamento. Numero totale=20.C. parapsilosis C. kefyr
C. glabrata S. cerevisiae C. hamulonii C. albicans
C. albicans (n°=6; f=30%) C. parapsilosis (n°=8; f=40%)
C. kefyr (n°=1; f=5%) C. glabrata (n°=2; f=10%)
Risultati, 73
In Figura 27 sono riportate le frequenze dei lieviti isolati dai campioni
costituiti da materiale vario, quali punte di cateteri o urine: C. albicans
(75%), C. tropicalis (13%), C. kefyr (4%), C. parapsilosis, C. krusei, C.
famata ed il lievito S. cerevisiae (2%).
Figura 27.
Distribuzione delle principali specie di lievito, isolate da materialidi varia natura (punte di cateteri, urine). Con n° è indicato il numero dei ceppi e con f la frequenza di isolamento. Numero totale=48.
C. albicans S. cerevisiae C. famata C. kefyr C. tropicalis C. krusei C. parapsilosis C. albicans (n°=36; f=75%) C. parapsilosis (n°=1; f=2%) C. krusei (n°=1; f=2%) C. tropicalis (n°=6; f=13%) C. kefyr (n°=2; f=4%) C. famata (n°=1; f=2%) S. cerevisiae (n°=1; f=2%)
Risultati, 74
3.2.1
Distribuzione dei principali ceppi di lievito esaminati
nei differenti siti corporei
L’analisi statistica dei dati relativi alla frequenza di isolamento delle
diverse specie di lievito identificate nei vari campioni biologici ha evidenziato
una significativa associazione tra la presenza di C. albicans nei campioni
respiratori (P=0,0053) e nei materiali di varia natura (P=0,0002), rispetto ad
emocolture e di questa specie nei materiali di varia natura, rispetto ai
campioni polimicrobici (P=0,0008) (Figura 28)
Figura 28. Confronto tra la distribuzione della specie C.albicans tra i campioni respiratori
e le emocolture (a), emocolture e materiali vari (b), campioni polimicrobici e materiali vari (c). Valori di P≤0,05 indicano una differenza statisticamente significativa.
C. albicans non-albicans
0
10
20
30
40
50
60
Campioni polimicrobici Materiali vari
Distretti
0
15
30
45
60
75
90
105
120
Campioni respiratori Emocolture
Distretti C. albicans non-albicans
0
10
20
30
40
50
60
Emocolture Materiali vari
Distretti C. albicans non-albicans **
P=0,0053
***P=0,0002
***P=0,0008
(a)
n ° c e p p i(b)
n ° c e p p i(c)
n ° c e p p iRisultati, 75
Al contrario, C. parapsilosis è stata isolata con significativa maggiore
frequenza tra i campioni di emocolture e da campioni polimicrobici rispetto a
materiali vari, con valori P=0,0003 e P=0,00013, rispettivamente (Figura
29).
0 10 20 30 40 50 60Emocolture Materiali vari
Distretti C. parapsilosis non-parapsilosis 0 10 20 30 40 50 60
Campioni polimicrobici Materiali vari
Distretti C. parapsilosis
non-parapsilosis
Figura 29.
Confronto tra la distribuzione della specie C. parapsilosis tra materiali vari e emocolture (a), tra materiali vari e campioni polimicrobici (b). Valori di P≤0,05 indicano una differenza statisticamente significativa.***
P=0,0003
***P=0,00013
(a)
n ° c e p p i(b)
n ° c e p p iRisultati, 76
Infine la specie C. glabrata ha mostrato una significativa prevalenza
nei campioni respiratori rispetto ai materiali vari e emocolture, con
rispettivamente P=0,0041 e P=0,00016 (Figura 30).
0 5 10 15 20 25 30 35 40Campioni respiratori Materiali vari
Distretti C. glabrata non-glabrata 0 10 20 30 40 50 60 70 80 90
Campioni respiratori Emocolture
Distretti C. glabrata
non-glabrata
Figura 30.
Confronto tra la distribuzione della specie C. glabrata tra materiali vari e campioni respiratori (a), tra emocolture e campioni respiratori (b). Valori di P≤0,05 indicano una differenza statisticamente significativa.3.3 SUSCETTIBILITÀ AI FARMACI ANTIFUNGINI
La valutazione della suscettibilità ai principali farmaci antifungini dei
ceppi, oggetto di studio, è stata effettuata utilizzando principalmente il
metodo in micro diluizione in brodo ( Sensititre® yeast one9).
Come riportato nei Materiali e Metodi (paragrafo 2.3.1), la piastra
Y09 ha permesso di saggiare la suscettibilità del lievito a 9 farmaci
antifungini: 5-fluorocitosina, amfotericina B, posaconazolo, voriconazolo,
itraconazolo, fluconazolo e le echinocandine anidulafungina, micafungina e
caspofungina.
**P=0,0041
***P=0,00016
(a)
n ° c e p p i(b)
n ° c e p p iRisultati, 77
Occasionalmente, per casi di difficile interpretazione o per necessità
di conferma sui risultati ottenuti mediante YO9 è stata utilizzata la metodica
di agar diffusione E-test.
In Tabella 6 sono riportati i risultati degli antimicogrammi eseguiti,
espressi come percentuale di sensibilità alle molecole antifungine, in
relazione al numero dei ceppi testati.
Tutti i ceppi di lievito isolati sono risultati essere suscettibili alle
echinocandine (anidulafungina, caspofungina, nicafungina), ad eccezione di
C. parapsilosis che ha mostrato una sensibilità del 13% verso micafungina
e di C. guilliermondii per la quale si è osservata una ridotta suscettibilità alla
caspofungina (1%).
Per quanto riguarda i farmaci azolici, C. krusei è risultata essere
resistente sia al fluconazolo, sia all’itraconazolo. Anche C. glabrata ha
mostrato una ridotta suscettibilità verso gli azoli, con solamente il 4% di
ceppi suscettibili al posaconazolo, 25% nei confronti del fluconazolo, 1%
verso l’itraconazolo, 3% verso il voriconazolo. Per C. parapsilosis è stata
osservata una suscettibilità nel 12% dei casi nei confronti di itraconazolo e
di voriconazolo.
La sensibilità delle specie di lievito saggiate in questo studio è
risultata essere del 100% nei confronti di 5-fluorocitosina, con l’eccezione di
C. krusei (1%) e C. tropicalis (6%).
Anche per quanto concerne il farmaco polienico amfotericina B, quasi
tutti i ceppi di lievito hanno mostrato una sensibilità totale, ad eccezione di
Risultati, 78
Tabella 6. Percentuali di sensibilità delle specie di lievito isolate, ai
principali farmaci antifungini.
Lievito isolato ANDa CASa MICAa FCb ABc POSd FZd IZd VORd
C. albicans (n°=97) 100% 100% 100% 100% 100% 60% 60% 58% 59% C. parapsilosis (n°=25) 100% 100% 13% 100% 100% 100% 100% 12% 12% C. krusei (n°=5) 100% 100% 100% 1% 100% 100% 0% 0% 100% C. tropicalis (n°=11) 100% 100% 100% 6% 100% 100% 100% 1% 100% C. kefyr (n°=4) 100% 100% 100% 100% 2% 100% 100% 100% 100% C. famata(n°=3) 100% 100% 100% 100% 1% 100% 100% 100% 100% C. guilliermondii (n°=2) 100% 1% 100% 100% 100% 100% 100% 0% 100% C. glabrata (n°=7) 100% 100% 100% 100% 100% 4% 25% 1% 3% C. dubliniensis (n°=4) 100% 100% 100% 100% 100% 100% 100% 100% 100% S. cerevisiae (n°=2) 100% 100% 100% 100% 100% 100% 100% 0% 100% C. utilis (n°= 1) 100% 100% 100% 100% 100% 100% 100% 0% 100% C. haemulonii (n°=1) 100% 100% 100% 100% 100% 100% 100% 100% 100% C. sphaerica (n° = 1) 100% 100% 100% 100% 100% 100% 0% 0% 100%
Gli antimicotici sono abbreviati con le seguenti sigle:
a
AND=anidulafungina, CAS=caspofungina, MICA=micafungina
b
FC=5-fluorocitosina
c
AB=amfotericina B
d
POS=posaconazolo, FZ=fluconazolo, IZ=itraconazolo, VOR=voriconazolo.
3.4 IDENTIFICAZIONE MOLECOLARE DELLE SPECIE
DEL GRUPPO “PSILOSIS”
3.4.1
Amplificazione del frammento del gene alcool
deidrogenasi secondaria (SADH)
Per ciascuno dei 23 ceppi di Candida parapsilosis sottoposti
all’identificazione molecolare, è stato estratto il DNA genomico, in base al
protocollo descritto nel paragrafo 2.4.1 (sezione”Materiali e Metodi”).
La qualità del DNA genomico estratto è stata valutata mediante
migrazione elettroforetica su gel d’agarosio (Figura 31, linee 1-12) e la
Risultati, 79
presenza nel gel medesimo di un marker di peso molecolare a
concentrazione nota (Figura 31, linea M) ha consentito di potere effettuare
una stima della concentrazione di DNA estratto per ciascun campione. Una
quantità di DNA genomico pari a 80 ng è stato impiegato nella reazione di
PCR, per amplificare una porzione del gene alcool deidrogenasi secondaria
(SADH), in tutti i ceppi esaminati, secondo il protocollo descritto nel
paragrafo 2.4.2.
Figura 31.
Esempio rappresentativo di DNA genomico estratto da 12 isolati clinici di C. parapsilosis, analizzati in questo lavoro di tesi (Linee1-12). M, marker di peso molecolare.In Figura 32 è riportato un esempio di amplificazione del frammento
SADH riferita a 9 ceppi di C. parapsilosis. Il marker di peso molecolare
(Figura 32, linea M) ha consentito di verificare la corretta amplificazione del
frammento, come dimostrato dalla presenza di una banda, in tutti i ceppi
presi in esame, del peso molecolare atteso di 716 paia di basi (Figura 32,
linee 1-9). Successivamente, i prodotti di amplificazione sono stati purificati
e sottoposti all’analisi di restrizione.
1 2 3 4 5 6 7 8 9 10 11 12 M bp
◄
4000
◄
10000
Risultati, 80
Figura 32.
Linee 1-9, profili di amplificazione del gene alcool deidrogenasisecondaria (SADH), ottenuti mediante PCR condotta su campioni di DNA genomico estratto da 9 ceppi di C. parapsilosis, oggetto dello studio. M, marker di peso molecolare. CN, controllo negativo.
3.4.2
Digestione del frammento SADH con l’enzima di
restrizione BanI ed identificazione delle specie del
gruppo “psilosis”
L’analisi della sequenza del frammento SADH amplificato nelle
specie del gruppo ”psilosis” presenta una diversa mappa di restrizione:
infatti mentre C. parapsilosis presenta un solo sito di taglio per l’enzima
Ban
I
, C. metapsilosis è caratterizzata dalla presenza nel frammento di tre
siti di restrizione, mentre per C. orthopsilosis non è presente alcun sito nella
sequenza del gene SADH (Tavanti et al., 2005).
Pertanto, i frammenti del gene SADH amplificati e purificati per tutti i
ceppi analizzati sono stati sottoposti a digestione enzimatica con l’enzima
Ban
I
, allo scopo di identificare l’eventuale presenza di C. metapsilosis e C.
orthopsilosis nella collezione di ceppi identificati come C. parapsilosis su
base biochimica.
1 2 3 4 5 6 7 8 9 CN M bp
◄
716
◄
1500
◄
500
◄
200
Risultati, 81
La migrazione elettroforetica dei prodotti di digestione ottenuti ha
consentito di mettere in evidenza i profili di restrizione. Per tutti quanti i
ceppi inclusi in questo studio è stata confermata l’identificazione ottenuta
mediante test biochimici, in quanto, come osservato in Figura 33, che
mostra un gel rappresentativo dei profili ottenuti dall’analisi di restrizione del
gene SADH, tutti i ceppi hanno mostrato un profilo compatibile con la
presenza di C. parapsilosis, specie con un solo sito di taglio per l’enzima
Ban
I
e caratterizzata dalla presenza di due frammenti di 521 e 196 bp.
Figura 33.
Esempi rappresentativi dei profili di restrizione ottenuti mediantedigestione enzimatica del frammento di PCR SADH con l’enzima BanI. Linee1-10 Candida parapsilosis. M=marker di peso molecolare.